水稻SBP 基因家族生物信息学分析

水稻SBP 基因家族生物信息学分析
摘要:SBP (squamosa promoter binding protein, SBP)基因家族是植物所特有的一类重要转录因子,广泛参与植物生长、发育以及多种生理生化反应的信号传导。水稻是目前为止基因组测序相当完整的一类植物,而且水稻也是现在人类生存赖以依存的粮食,因此水稻早已成为分子生物学研究的重点对象,进行水稻基因组信息挖掘与分析对于水稻功能基因组学的发展具有重要意义。本实验以植物(水稻)特异转录因子SBP基因家族为实例,讲述如何利用生物信息数据库资源和软件工具,对该基因家族进行分析。本章所用数据主要来自北京大学生物信息中心(https://www.360docs.net/doc/3416133138.html,/chinese/)构建的植物转录因子数据库,研究对象主要为水稻基因组中 29个SBP转录因子基因。所用生物信息学工具包括基因结构显示、双序列比对、蛋白质功能域识别、蛋白质保守域预测、序列图标构建、多序列比对、系统发育树构建、,以及蛋白质二级、三维结构空间图形显示等。本实验结果均为水稻SBP 基因家族的进一步功能分析提供了重要研究基础。
关键词:水稻、SBP家族、生物信息学
引言:我们知道,转录前调控、转录调控和转录后调控是真核生物基因表达调控的重要组成部分,其中转录调控通过顺式作用元件和反式作用因子相互作用实现。顺式作用元件(cis-element)泛指 DNA 序列一个片段,通常位于被调控基因的上游,主要包括启动子(promoter)、增强子(enhancer)和抑制子(suppressor)三类。反式作用因子泛指与顺式作用元件直接或间接结合
并参与靶基因转录过程的调控因子,通称转录因子(transcription factor)。转录因子可以分为两大类,即通用转录因子(general transcription factor)和特异转录因子(specific transcription factor)。通用转录因子与靶基因上游约 10-35 位的 TATA 框(TATA-box)或启动子区域转录起始位点(transcription start site)DNA序列结合,并与 II型 RNA聚合酶一起,形成转录起始复合物。特异转录因子种类繁多、功能复杂,它们与靶基因上游各种特定 DNA序列片段结合,激活或抑制靶基因转录活性,以调控靶基因在不同组织、不同细胞、不同环境条件下特异表达。如无特别说明,通常所说的转录因子即指特异转录因子。
一、结果与分析
1.水稻SBP的挖掘
先到Pfam 数据库中去搜索SBP 结构域(domain), 其标识号应该是xxx(PF03110), 获取它的HMM 序列文件。从TIGR 水稻数据库(https://www.360docs.net/doc/3416133138.html,, The TIGR Rice Database release 6.0)下载水稻基因组12条染色体的蛋白质序列。然后利用基于隐马尔科夫模型的HMMER 程序(版本3.0)来搜索, E <=10-10的序列被认为是水稻中的含有SBP 结构域的候选序列(共31条)。再利用SMART在线工具分析结构域, 把没有显示SBP 结构域蛋白除掉(3条), 最后得到水稻的SPB基因基因家族成员。
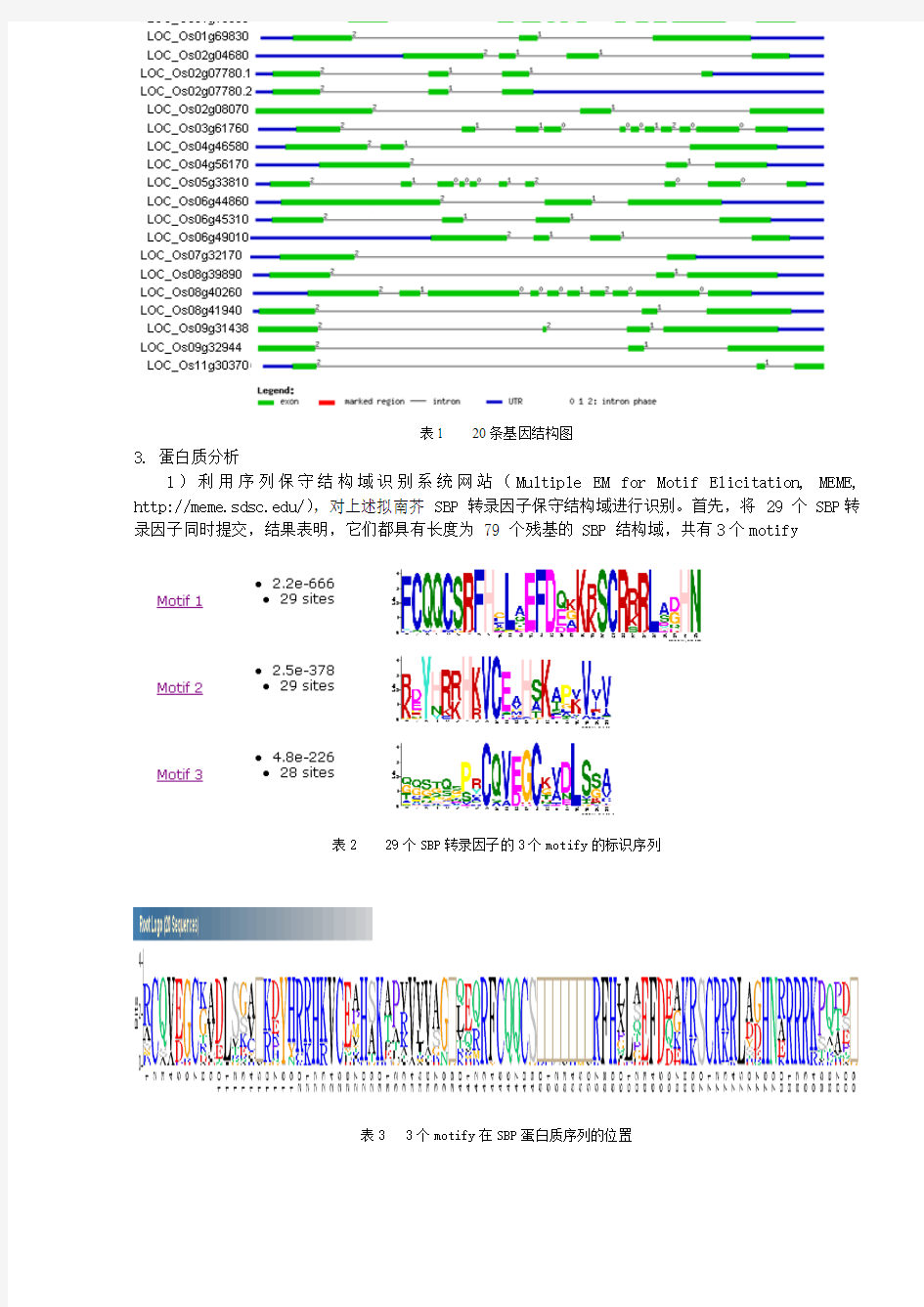
2.基因结构分析
将从TAIR获得的水稻SPB家族基因的CDS序列和对应的全基因组序列, 利用Gene Structure Display Server(https://www.360docs.net/doc/3416133138.html,/)绘出基因结构图
表1 20条基因结构图
3. 蛋白质分析
1)利用序列保守结构域识别系统网站(Multiple EM for Motif Elicitation, MEME, https://www.360docs.net/doc/3416133138.html,/),对上述拟南芥 SBP 转录因子保守结构域进行识别。首先,将 29 个 SBP转录因子同时提交,结果表明,它们都具有长度为 79 个残基的 SBP 结构域,共有3个motify
表2 29个SBP转录因子的3个motify的标识序列
表3 3个motify在SBP蛋白质序列的位置
2)二级结构分析
二级结构是指不同氨基酸间C=O 和N-H 基团间的氢键形成的稳定结构,主要为α- 螺旋和β- 折叠。利用SOPMA 程序(http://npsa-pbil.ibcp.fr/cgi-bin/npsa_automat.pl?page=npsa.sopma.html)对水稻29 条SBP家族蛋白质序列二级结构进行预测,结果发现有21条蛋白质序列的二级结构不同,所有的氨基酸序列都以随机卷曲为主要组成部分,其次就是α-螺旋。
α-螺旋延伸链β-折叠无规卷曲
LOC_Os01g18850 37.24% 13.57% 3.83% 45.36%
LOC_Os01g69830 20.15% 19.17% 8.25% 52.43%
LOC_Os02g08070.131.44% 15.72% 9.17% 43.67%
LOC_Os02g04680.218.38% 12.82% 2.14% 66.67%
LOC_Os02g04680.116.20% 14.93% 3.62% 65.25%
LOC_Os02g07780.221.37% 15.38% 6.84% 56.41%
LOC_Os02g07780.120.72% 17.13% 7.97% 54.18%
LOC_Os03g6176037.05% 12.69% 5.26% 44.99%
LOC_Os04g4658026.11% 10.28% 4.72% 58.89%
LOC_Os04g5617034.38% 14.18% 8.11% 43.03%
LOC_Os05g3381032.78% 16.15% 6.53% 44.54%
LOC_Os06g44860 31.92% 15.02% 7.98% 45.07%
LOC_Os06g4901016.42% 17.47% 4.63% 61.47%
LOC_Os06g4531031.78% 11.08% 6.71% 50.44%
LOC_Os07g3217032.87% 8.33% 8.33% 50.46%
LOC_Os08g3989017.99% 8.87% 7.91% 65.23%
LOC_Os08g4194023.52% 16.92% 6.59% 52.97%
LOC_Os08g4026034.12% 12.19% 4.82% 48.86%
LOC_Os09g3294422.88% 15.47% 4.45% 57.20%
LOC_Os09g3143814.25% 11.75% 4.75% 69.25%
LOC_Os11g3037031.82% 9.09% 5.11% 53.98%
表3 21条氨基酸序列的二级结构的组成
3)三级结构分析
蛋白质空间结构模型通过Swiss-Model (http://swiss https://www.360docs.net/doc/3416133138.html,)建立。通过Swiss-Model 对葡萄的45 条氨基酸序列进行三维结构同源建模,结果表明它们绝大多数具有十分相似的三维结构。例如:
LOC_Os01g18850.1 LOC_Os06g45310.1 LOC_Os11g30370.1
4.进化树构建
利用MAGE对21条SBP结构域序列做分子进化分析
讨论
以SBP 蛋白保守区氨基酸序列为信息探针,从水稻数据库中检索到SBP 转录因子相应的蛋白序列,成功地利用生物信息学数据库和软件工具,对水稻SBP 转录因子家族基因结构和蛋白质结构等进行了分析,从中得到该转录因子家族不同成员之间的相互关系和演化历程,至于其生物学功能,还需要在葡萄中进行克隆以及表达分析来验证。目前,从高等植物中已分离鉴定的转录因子有数千种,已经证明其中相当一部分在调节植物的生长发育及其对外界环境的反应等方面起着重要的作用。不仅如此,还发现一个逆境相关转录因子可以调控多个逆境相关功能基因的表达,在利用转录因子来改良植物抗逆性方面效果显著。因此,植物转录因子一直是现在生物学研究领域的热点。从TAIR获得水稻SBP 转录因子相应的蛋白序列,成功地利用生物信息学数据库和软件工具,对水稻SBP 转录因子家族基因结构和蛋白质结构等进行了分析,从中得到该转录因子家族不同成员之间的相互关系和演化历程,至于其生物学功能,还需要在水稻中进行克隆以及表达分析来验证,因此,该研究就为下一步研究水稻转录因子的生物学功能提供了参考依据。
参考文献:
[1]曹雪,上官凌飞,于华平,杨光,王晨,谭洪花,房经贵,葡萄SBP基因家族生物信息学分析,南京农业大学园艺学
院,南京, 210095,基因组学与应用生物学, 2010年,第29卷,第4期,第791-798页
[2]罗静初,拟南芥SBP 转录因子基因家族分析,北京大学
【高中生物】功能基因的克隆及生物信息学分析
(生物科技行业)功能基因的克隆及生物信息学分析
功能基因的克隆及其生物信息学分析 摘要:随着多种生物全基因组序列的获得,基因组研究正从结构基因组学(structuralgenomics)转向功能基因组学(functionalgenomics)的整体研究。功能基因组学利用结构基因组学研究获得的大量数据与信息评价基因功能(包括生化功能、细胞功能、发育功能、适应功能等),其主要手段结合了高通量的大规模的实验方法、统计和计算机分析技术[1],它代表了基因分析的新阶段,已成为21世纪国际生命科学研究的前沿。功能基因组学是利用基因组测序获得的信息和产物,发展和应用新的实验手段,通过在基因组或系统水平上全面分析基因的功能,使生物学研究从对单一基因或蛋白的研究转向多个基因或蛋白同时进行系统的研究,是在基因组静态的组成序列基础上转入对基因组动态的生物学功能学研究[2]。如何研究功能基因,也成为我们面临的一个课题,本文就克隆和生物信息学分析在研究功能基因方面的应用做一个简要的阐述。 关键词:功能基因、克隆、生物信息学分析。 1.功能基因的克隆 1.1图位克隆方法 图位克隆又称定位克隆,它是根据目标基因在染色体上确切位置,寻找与其紧密连锁的分子标记,筛选BCA克隆,通过染色体步移法逐步逼近目的基因区域,根据测序结果或用BAC、YAC克隆筛选cDNA表达文库寻找候选基因,得到候选基因后再确定目标基因。优点是无需掌握基因产物的任何信息,从突变体开始,逐步找到基因,最后证实该基因就是造成突变的原因。通过图位克隆许多
控制质量性状的单基因得以克隆,最近也有报道某些控制数量性状的主效基因(控制蕃茄果实大小的基因克隆[3]、控制水稻成熟后稻谷脱落基因克隆[4]以及小麦VRN2基因克隆[5]等)也通过图位克隆法获得。 1.2同源序列克隆目的基因 首先根据已知的基因序列设计PCR引物,在已知材料中扩增到该片段,并经克隆测序验证,利用放射性同位素标记或其他非同位素标记该PCR片段作为探针,与待研究材料的cDNA文库杂交,就可以获得该基因cDNA克隆,利用克隆进一步筛选基因组文库,挑选阳性克隆,亚克隆并测序,从中就可以筛选到该基因的完整序列。 1.3结合连锁和连锁不平衡的分析方法 结合连锁和连锁不平衡的分析方法是未知基因克隆研究领域发展的新方向[6]。(Linkagedisequilibrium,LD)。与连锁分析不同,连锁不平衡分析可以利用自然群体中历史发生的重组事件。历史上发生的重组使连锁的标记渐渐分布到不同的同源染色体上,这样就只有相隔很近的标记才能不被重组掉,从而形成大小不同的单倍型片段(Haplotypeblock)。这样经过很多世代的重组,只有相隔很近的基因,才能仍处在相同的原始单倍型片段上,基因间的连锁不平衡才能依然存在。所以基于连锁不平衡分析,可以实现目的基因的精细定位。林木大多为自由授粉的异交物种,所以连锁不平衡程度很低,林木基因组中的LD可能会仅局限于非常小的区域,这就为目的基因的精细定位提供了可能,结合SNP检测技术,科学家甚至可以将效应位点直接与单个的核苷酸突变关联起来,进行数量性状寡核苷酸
高通量测序生物信息学分析(内部极品资料,初学者必看)
基因组测序基础知识 ㈠De Novo测序也叫从头测序,是首次对一个物种的基因组进行测序,用生物信息学的分析方法对测序所得序列进行组装,从而获得该物种的基因组序列图谱。 目前国际上通用的基因组De Novo测序方法有三种: 1. 用Illumina Solexa GA IIx 测序仪直接测序; 2. 用Roche GS FLX Titanium直接完成全基因组测序; 3. 用ABI 3730 或Roche GS FLX Titanium测序,搭建骨架,再用Illumina Solexa GA IIx 进行深度测序,完成基因组拼接。 采用De Novo测序有助于研究者了解未知物种的个体全基因组序列、鉴定新基因组中全部的结构和功能元件,并且将这些信息在基因组水平上进行集成和展示、可以预测新的功能基因及进行比较基因组学研究,为后续的相关研究奠定基础。 实验流程: 公司服务内容 1.基本服务:DNA样品检测;测序文库构建;高通量测序;数据基本分析(Base calling,去接头, 去污染);序列组装达到精细图标准 2.定制服务:基因组注释及功能注释;比较基因组及分子进化分析,数据库搭建;基因组信息展 示平台搭建 1.基因组De Novo测序对DNA样品有什么要求?
(1) 对于细菌真菌,样品来源一定要单一菌落无污染,否则会严重影响测序结果的质量。基因组完整无降解(23 kb以上), OD值在1.8~2.0 之间;样品浓度大于30 ng/μl;每次样品制备需要10 μg样品,如果需要多次制备样品,则需要样品总量=制备样品次数*10 μg。 (2) 对于植物,样品来源要求是黑暗无菌条件下培养的黄化苗或组培样品,最好为纯合或单倍体。基因组完整无降解(23 kb以上),OD值在1.8~2.0 之间;样品浓度大于30 ng/μl;样品总量不小于500 μg,详细要求参见项目合同附件。 (3) 对于动物,样品来源应选用肌肉,血等脂肪含量少的部位,同一个体取样,最好为纯合。基因组完整无降解(23 kb以上),OD值在1.8~2.0 之间;样品浓度大于30 ng/μl;样品总量不小于500 μg,详细要求参见项目合同附件。 (4) 基因组De Novo组装完毕后需要构建BAC或Fosmid文库进行测序验证,用于BAC 或Fosmid文库构建的样品需要保证跟De Novo测序样本同一来源。 2. De Novo有几种测序方式 目前3种测序技术 Roche 454,Solexa和ABI SOLID均有单端测序和双端测序两种方式。在基因组De Novo测序过程中,Roche 454的单端测序读长可以达到400 bp,经常用于基因组骨架的组装,而Solexa和ABI SOLID双端测序可以用于组装scaffolds和填补gap。下面以solexa 为例,对单端测序(Single-read)和双端测序(Paired-end和Mate-pair)进行介绍。Single-read、Paired-end和Mate-pair主要区别在测序文库的构建方法上。 单端测序(Single-read)首先将DNA样本进行片段化处理形成200-500bp的片段,引物序列连接到DNA片段的一端,然后末端加上接头,将片段固定在flow cell上生成DNA簇,上机测序单端读取序列(图1)。 Paired-end方法是指在构建待测DNA文库时在两端的接头上都加上测序引物结合位点,在第一轮测序完成后,去除第一轮测序的模板链,用对读测序模块(Paired-End Module)引导互补链在原位置再生和扩增,以达到第二轮测序所用的模板量,进行第二轮互补链的合成测序(图2)。 图1 Single-read文库构建方法图2 Paired-end文库构建方法
生物信息学软件及使用概述
生物信息学软件及使 刘吉平 liujiping@https://www.360docs.net/doc/3416133138.html, 用概述 生 物秀-专心做生物! w w w .b b i o o .c o m
生物信息学是一门新兴的交叉学生物信息学的概念: 科,它将数学和计算机知识应用于生物学,以获取、加工、存储、分类、检索与分析生物大分子的信息,从而理解这些信息的生物学意义。 生 物秀-专心做生物! w w w .b b i o o .c o m
分析和处理实验数据和公共数据,生物信息学软件主要功能 1.2.提示、指导、替代实验操作,利用对实验数据的分析所得的结论设计下一阶段的实验 3.实验数据的自动化管理 4.寻找、预测新基因及其结构、功能 5.蛋白质高级结构及功能预测(三维建模,目前研究的焦点和难点) 生 物秀-专心做生物! w w w .b b i o o .c o m
功能1. 分析和处理实验数据和公共数据,加快研究进度,缩短科研时间 ?核酸:序列同源性比较,分子进化树构建,结构信息分析,包括基元(Motif)、酶切点、重复片断、碱基组成和分布、开放阅读框(ORF ),蛋白编码区(CDS )及外显子预测、RNA 二级结构预测、DNA 片段的拼接; ?蛋白:序列同源性比较,结构信息分析(包括Motif ,限制酶切点,内部重复序列的查找,氨基酸残基组成及其亲水性及疏水性分析),等电点及二级结构预测等等; ?本地序列与公共序列的联接,成果扩大。 生 物秀-专心做生物! w w w .b b i o o .c o m
Antheprot 5.0 Dot Plot 点阵图 Dot plot 点阵图能够揭示多个局部相似性的复杂关系 生 物秀-专心做生物! w w w .b b i o o .c o m
JMJD2B基因的生物信息学分析
JMJD2B基因的生物信息学分析 2006级本硕一班谢泽飞 指导老师:吴炳礼,许丽艳,李恩民 一对该基因的初步认识 JMJD2B基因是JMJB2基因家族中的一员,而说到该基因的来龙去脉还得从它的家族谈起。JMJD2家族是通过体外克隆的方式从一个编号为KIAA0867的人脑分粒cDNA文库中获得的,而且通过与JMJD1C基因的比较,更加明确了该基因家族的结构特点。该基因家族主要含有一个JmjN,JmjC,JD2H功能域,两个TUDOR功能域。有趣的是在该基因家族的C端末尾的第二个TUDOR功能域上有一个双向的出核入核定位信号,而这似乎提示了某些问题。现在我们对这整个家族有了一个初步的认识,再来看JMJD2B这个基因: 定位:19p13.3 全长:1096 AA 分子量:121896 Da 等电点:6.79 含有2个锌指结构,均为PHD型: 731-789 MCFTSGGENT EPLPANSYIG DDGTSPLIAC GKCCLQVHAS CYGIRPELVN EGWTCSRCA 851-907 KCVYCRKRMK KVSGACIQCS YEHCSTSFHV TCAHAAGVLM EPDDWPYVVS ITCLKHK 在15-57 处含有JmjN功能域,146-309含有JmjC功能域. 二该基因的主要生物学功能 第一点,通过进化树的分析,显示该基因在马这一动物中高度保守。
通过分析该基因的序列,在数据库中查找其同源序列,进而选取不同物种的代表基因进行进化树分析,我们可以看到,马这个物种的被归到了低等的昆虫中去了,按照进化的理论,应该不会出现这种情况的,于是,我们推断,该基因在马这个物种中特别保守,所以进化中的变异非常的小。再进一步想,该基因对马这个物种可能是很重要的,那么为什么这个基因会如此重要呢?通过查找文献,我得出下面的另一个结论,就是该基因的生物学功能:该基因具有去甲基化作用。当然,由于实验不是在马身上做的,我们也就只能得出一般性的结论。 第二点,参与组蛋白去甲基的作用,主动且有普遍特异性。 很显然,越来越多的研究表明,在真核细胞中组蛋白的甲基化修饰水平是该细胞的表观遗传的活跃程度的一个很重要指标。而JMJD2B的这个功能的意义是重大的,其能够使染色体核周异染色体的核周组蛋白去甲基化,进而对细胞的遗传进行表观遗传的调控。研究人员利用间接荧光免疫法进行追踪发现,在两组对照的雌鼠JMJD2B-GFP底物系统中,JMJD2B基因过度表达的一组,H3K9me3水平明显低于另外正常的那一组,都转变为H3K9me1的构型,这说明了JMJD2B 的特异去甲基作用,而且这一过程是主动的,都发生在细胞染色体复制前的一瞬间,速度非常快。但是,在巨大组蛋白中,该基因有表现出可以同时参与H3K9me3和H3K9me2的去甲基作用。
生物信息学分析实践
水稻瘤矮病毒(RGDV)外层衣壳蛋白 P8的同源模建 高芳銮(Raindy) 同源模建(homology modeling) ,也叫比较模建(Compatative modeling),其前提是一个或多个同源蛋白质的结构已知,当两个蛋白质的序列同源性高于35%,一般情况下认为它们的三维结构基本相同;序列同源性低于30%的蛋白质难以得到理想的结构模型。同源模建是目前最为成功且实用的蛋白质结构预测方法, SWISS-MODEL 是由SwissProt 提供的目前最著名的蛋白质三级结构预测服务器,创建于1993年,面向全世界的生物化学与分子生物学研究工作者提供免费的自动模建服务。SWISS-MODEL 服务器提供的同源模建有两种工作模式:首选模式(First Approach mode)和 项目模式(Project mode)。 本实例以RGDV P8蛋白为研究对象采用首选模式进行同源模建。 图1 SWISS-MODEL 的主界面 操作流程如下: 1.选择模式 单击左侧的“MENU ”菜单下方的“First Approach mode ”,右侧窗口自动SWISS-MODEL 工作窗口,在相应文本框中分别输入的E-mail 、项目标题、待模建的蛋白质序列,SWISS-MODEL 支持以FASTA 格式直接输入或提交UniProt 的登录号,如图2所示。 《生物信息学分析实践》样 稿
图2 SWISS-MODEL 的序列提交页面 2.参数设置 当前版本只有一个选项可设置,如果用户需要使用指定的模板,可在“Use a specific template ”后的输入框填入ExPDB 晶体图像数据库中的模板代码,其格式为“PDBCODE+ChainID ”,如“1uf2P ”。本例不使用指定模板,默认留空。完毕,点击“Submit Modeling Request ”提交模建请求,服务器返回提交成功的提示,如图3所示: 图3 成功提交 SWISS-MODEL WORKSPACEW 页面会自动刷新,直至模建完成,如图4所示,同时模建结果也会发送到指定的邮箱。 3结果解读 点击下图右上方的“Print/Save this page as ”后的图标,可以将整个结果以PDF 文档格式保存到本地计算机中。模建结果给出了五个部分的信息:模建详情(Model Details)、比对信息(Alignment)、模建评价 (Anolea/Gromos/Verify3D)、模建日志(Modelling log)、模板选择日志(Template Selection Log)。 《生物信息学分析实践》样稿
生物信息学考试试卷修订稿
生物信息学考试试卷 WEIHUA system office room 【WEIHUA 16H-WEIHUA WEIHUA8Q8-
一、名词解释(每小题4分,共20分) 1、生物信息学 广义:生命科学中的信息科学。生物体系和过程中信息的存贮、传递和表达;细胞、组织、器官的生理、病理、药理过程的中各种生物信息。 狭义:生物分子信息的获取、存贮、分析和利用。 2、人类基因组计划 人类基因组计划准备用15年时间,投入30亿美元,完成人类全部24条染色体的3×109脱氧核苷酸对(bp)的序列测定,主要任务包括作图(遗传图谱、物理图谱的建立及转录图谱的绘制)、测序和基因识别。其中还包括模式生物(如大肠杆菌、酵母、线虫、小鼠等)基因组的作图和测序,以及信息系统的建立。作图和测序是基本的任务,在此基础上解读和破译生物体生老病死以及和疾病相关的遗传信息。 3、蛋白质的一级结构 蛋白质的一级结构是指多肽链中氨基酸的序列 4、基因 基因--有遗传效应的DNA片断,是控制生物性状的基本遗传单位。 5、中心法则 是指遗传信息从传递给,再从RNA传递给,即完成遗传信息的转录和翻译的过程。也可以从DNA传递给DNA,即完成DNA的复制过程。这是所有有细胞结构的生物所遵循的法则。 6 、DNA序列比较 序列比较的根本任务是:(1)发现序列之间的相似性;(2)辨别序列之间的差异 目的: 相似序列相似的结构,相似的功能 判别序列之间的同源性 推测序列之间的进化关系 7、一级数据库 数据库中的数据直接来源于实验获得的原始数据,只经过简单的归类整理和注释 8、基因识别 基因识别,是生物信息学的一个重要分支,使用生物学实验或计算机等手段识别DNA序列上的具有生物学特征的片段。基因识别的对象主要是蛋白质编码基因,也包括其他具有一定生物学功能的因子,如RNA基因和调控因子。 9、系统发生学 系统发生学(phylogenetics)——研究物种之间的进化关系。 10、基因芯片 基因芯片(gene chip),又称DNA微阵列(microarray),是由大量cDNA或寡核苷酸探针密集排列所形成的探针阵列,其工作的基本原理是通过杂交检测信息。
生物信息学概论
2013/5/23
生物信息学概论
2013-5
提纲
1. 发展简史 2. 主要研究领域 3. 软件和工具
1. 发展简史
1946年 1946 年
美国生产出第一台全自动电子数字计算机“埃尼阿克”
1
2013/5/23
1. 发展简史
1955年 1955 年
Frederick Sanger determined the complete amino acid sequence of insulin in 1955 and earned him his first Nobel prize in Chemistry in 1958.
1. 发展简史
1965年 1965 年
The first Atlas of Protein Sequence and Structure contained sequence information on 65 proteins.
Dr. Margaret Oakley Dayhoff (1925-1983) was a pioneer in the use of computers in chemistry and biology, beginning with her PhD thesis project in 1948. Her work was multi-disciplinary, and used her knowledge of chemistry, mathematics, biology and computer science to develop an entirely new field. She is credited today as a founder of the field of Bioinformatics.
1. 发展简史
1965年 1965 年
First use of molecular sequences for evolutionary studies
One of the founding fathers of the field of molecular evolution
Zuckerkandl, E. and Pauling, L. (1965). "Molecules as documents of evolutionary history." Journal of theoretical biology 8(2): 357.
2
最新生物信息学考试复习
——古A.名词解释 1. 生物信息学:广义是指从事对基因组研究相关的生物信息的获取,加工,储存,分配,分析和解释。狭义是指综合应用信息科学,数学理论,方法和技术,管理、分析和利用生物分子数据的科学。 2. 基因芯片:将大量已知或未知序列的DNA片段点在固相载体上,通过物理吸附达到固定化(cDNA芯片),也可以在固相表面直接化学合成,得到寡聚核苷酸芯片。再将待研究的样品与芯片杂交,经过计算机扫描和数据处理,进行定性定量的分析。可以反映大量基因在不同组织或同一组织不同发育时期或不同生理条件下的表达调控情况。 3. NCBI:National Center for Biotechnology Information.是隶属于美国国立医学图书馆(NLM)的综合性数据库,提供生物信息学方面的研究和服务。 4. EMBL:European Molecular Biology Laboratory.EBI为其一部分,是综合性数据库,提供生物信息学方面的研究和服务。 5. 简并引物:PCR引物的某一碱基位置有多种可能的多种引物的混合体。 6. 序列比对:为确定两个或多个序列之间的相似性以至于同源性,而将它们按照一定的规律排列。
7. BLAST:Basic Local Alignment Search Tool.是通过比对(alignment)在数据库中寻找和查询序列(query)相似度很高的序列的工具。 8. ORF:Open Reading Frame.由起始密码子开始,到终止密码子结束可以翻译成蛋白质的核酸序列,一个未知的基因,理论上具有6个ORF。 9. 启动子:是RNA聚合酶识别、结合并开始转录所必须的一段DNA序列。原核生物启动子由上游调控元件和核心启动子组成,核心启动子包括-35区(Sextama box)TTGACA,-10区(Pribnow Box)TATAAT,以及+1区。真核生物启动子包括远上游序列和启动子基本元件构成,启动子基本元件包括启动子上游元件(GC岛,CAAT盒),核心启动子(TATA Box,+1区帽子位点)组成。 10. motif:模体,基序,是序列中局部的保守区域,或者是一组序列中共有的一小段序列模式。 11. 分子进化树:通过比较生物大分子序列的差异的数值重建的进化树。 12. 相似性:序列比对过程中用来描述检测序列和目标序列之间相似DNA碱基或氨基酸残基序列所占的比例。 13. 同源性:两个基因或蛋白质序列具有共同祖先的结论。
生物信息学的主要研究内容
常用数据库 在DNA序列方面有GenBank、EMBL和等 在蛋白质一级结构方面有SWISS-PROT、PIR和MIPS等 在蛋白质和其它生物大分子的结构方面有PDB等 在蛋白质结构分类方面有SCOP和CATH等 生物信息学的主要研究内容 1、序列比对(Alignment) 基本问题是比较两个或两个以上符号序列的相似性或不相似性。序列比对是生物信息学的基础,非常重要。两个序列的比对有较成熟的动态规划算法,以及在此基础上编写的比对软件包BLAST和FASTA,可以免费下载使用。这些软件在数据库查询和搜索中有重要的应用。 2、结构比对 基本问题是比较两个或两个以上蛋白质分子空间结构的相似性或不相似性。已有一些算法。 3、蛋白质结构预测,包括2级和3级结构预测,是最重要的课题之一 从方法上来看有演绎法和归纳法两种途径。前者主要是从一些基本原理或假设出发来预测和研究蛋白质的结构和折叠过程。分子力学和分子动力学属这一范畴。后者主要是从观察和总结已知结构的蛋白质结构规律出发来预测未知蛋白质的结构。同源模建(Homology)和指认(Threading)方法属于这一范畴。虽然经过30余年的努力,蛋白结构预测研究现状远远不能满足实际需要。 4、计算机辅助基因识别(仅指蛋白质编码基因)。最重要的课题之一 基本问题是给定基因组序列后,正确识别基因的范围和在基因组序列中的精确位置.这是最重要的课题之一,而且越来越重要。经过20余年的努力,提出了数十种算法,有十种左右重要的算法和相应软件上网提供免费服务。原核生物计算机辅助基因识别相对容易些,结果好一些。从具有较多内含子的真核生物基因组序列中正确识别出起始密码子、剪切位点和终止密码子,是个相当困难的问题,研究现状不能令人满意,仍有大量的工作要做。 5、非编码区分析和DNA语言研究,是最重要的课题之一 在人类基因组中,编码部分进展总序列的3~5%,其它通常称为“垃圾”DNA,其实一点也不是垃圾,只是我们暂时还不知道其重要的功能。分析非编码区DNA 序列需要大胆的想象和崭新的研究思路和方法。DNA序列作为一种遗传语言,不仅体现在编码序列之中,而且隐含在非编码序列之中。 6、分子进化和比较基因组学,是最重要的课题之一 早期的工作主要是利用不同物种中同一种基因序列的异同来研究生物的进化,构建进化树。既可以用DNA序列也可以用其编码的氨基酸序列来做,甚至于可通过相关蛋白质的结构比对来研究分子进化。以上研究已经积累了大量的工作。近年来由于较多模式生物基因组测序任务的完成,为从整个基因组的角度来研究分子进化提供了条件。 7、序列重叠群(Contigs)装配 一般来说,根据现行的测序技术,每次反应只能测出500或更多一些碱基对的序列,这就有一个把大量的较短的序列全体构成了重叠群(Contigs)。逐步把它们拼接起来形成序列更长的重叠群,直至得到完整序列的过程称为重叠群装配。拼接EST数据以发现全长新基因也有类似的问题。已经证明,这是一个NP-完备
生物信息学分析
4、生物信息学分析 通过核苷酸序列数据库和基因序列同源性在线分析途径初步对Rv2029c基因进行分类整理。由于结核分枝杆菌耐利福平野生株与核苷酸序列数据库KEGG GENES中的结核分枝杆菌标准株H37Rv的匹配率为100%,以下对基因的分析按照结核分枝杆菌标准株H37Rv的数据库信息进行,即完全匹配的1020bp长度序列(本次提取基因中包含上下游引物等序列,较长,1346bp)。 4.1基本信息 表1 基因基本信息 4.2基因组信息 表2 基因组信息
5、PLN02341(PfkB型碳水化合物激酶家族蛋白),位点208-294 6、PTZ0029(核糖激酶),位点205-301 药物靶点1、同源基因没有药物靶点 2、非同源但序列相似基因没有药物靶点 图3 蛋白结构域 4.3蛋白表达 4.3.1 二级结构分析 预测结果显示,PfkB蛋白的二级结构中β转角占46.61%,α螺旋占33.63%,β折叠占19.76%。转角结构和螺旋结构构成了结核分枝杆菌PfkB蛋白二级结构的骨架。
图4 蛋白二级结构 4.3.2 跨膜区分析 Tuberculist跨膜蛋白预测结果表明:蛋白长度339aa,预测跨膜蛋白数0。 图5 蛋白跨膜区分析 4.3.3 信号肽预测 Predict Protein分析表明PfkB蛋白氨基酸残基没有信号肽,由此推断此蛋白不包含信号肽,不是分泌型蛋白质。
图6 蛋白信号肽预测 4.3.4 疏水性分析 分析结果显示,蛋白最大疏水指数为2.411,最小疏水指数为-2.372。
图7 蛋白疏水性分析 4.3.5 DNA同源性分析 表3 基因同源性分析 菌株序列覆盖 率 E值一致性 Mycobacterium tuberculosis strain Beijing-like, complete genome 100% 0.0 100% Mycobacterium bovis subsp. bovis AF2122/97 complete genome 100% 0.0 100% Mycobacterium tuberculosis 18b genome 100% 0.0 100% Mycobacterium tuberculosis H37RvSiena, complete genome 100% 0.0 100% Mycobacterium tuberculosis str. Kurono DNA, complete genome 100% 0.0 100% Mycobacterium tuberculosis 49-02 complete 100% 0.0 100%
蛋白质组学生物信息学分析介绍
生物信息学分析FAQ CHAPTER ONE ABOUT GENE ONTOLOGY ANNOTATION (3) 什么是GO? (3) GO和KEGG注释之前,为什么要先进行序列比对(BLAST)? (3) GO注释的意义? (3) GO和GOslim的区别 (4) 为什么有些蛋白没有GO注释信息? (4) 为什么GO Level 2的统计饼图里蛋白数目和差异蛋白总数不一致? (4) 什么是差异蛋白的功能富集分析&WHY? (4) GO注释结果文件解析 (5) Sheet TopBlastHits (5) Sheet protein2GO/protein2GOslim (5) Sheet BP/MF/CC (6) Sheet Level2_BP/Level2_MF/Level2_CC (6) CHAPTER TWO ABOUT KEGG PATHWAY ANNOTATION (7) WHY KEGG pathway annotation? (7) KEGG通路注释的方法&流程? (7) KEGG通路注释的意义? (7) 为什么有些蛋白没有KEGG通路注释信息? (8) 什么是差异蛋白的通路富集分析&WHY? (8) KEGG注释结果文件解析 (8) Sheet query2map (8) Sheet map2query (9) Sheet TopMapStat (9) CHAPTER THREE ABOUT FEATURE SELECTION & CLUSTERING (10) WHY Feature Selection? (10)
聚类分析(Clustering) (10) 聚类结果文件解析 (10) CHAPTER FOUR ABOUT PROTEIN-PROTEIN INTERACTION NETWORK (12) 蛋白质相互作用网络分析的意义 (12) 蛋白质相互作用 VS生物学通路? (12) 蛋白质相互作用网络分析结果文件解析 (12)
生物信息学分析
生物信息学分析 生物信息学难吗? 经常有人向我问这个问题,这有什么疑问吗?如果不难学,根本就不用问我这个问题。也无需投入那么多时间精力就能掌握,更无需花费三四千元参加线下的培训班,也不会月薪过万。所以,答案很肯定,道理很简单:生物信息比较难学。 为什么难学? 我总结里几点原因。首先,这是一个交叉学科,要求你既要有生物学的基础,又要有很强的计算机操作技能。这个就有点困难了。因为只是一个生物学就包括多个门类,有很多东西需要去学习,还需要学习计算机知识。很多人一门内容还没学明白,现在还得在加一门,这就属于祸不单行,雪上加霜,屋漏偏逢连夜雨。因此,这种既懂生物学,又懂计算机的复合型人才就比较短缺。而且,生物信息本质上属于数据挖掘,除了生物,计算机,到后面还需要极强的统计学知识才能做好数据分析,所以,还得加上统计学,也就是生物信息学=生物学+计算机科学+统计学三门学科的知识,这也就是为什么生物信息学比较难学。 第二个原因,生物信息本身就包括很多内容,比如DNA的分析,RNA的分析,甲基化的分析,蛋白质的分析等方面,每一
门类又完全不同,从物种方面来分,动物,植物,微生物,医学等有差别很大,很难有一劳永逸,放之四海而皆准的分析方法。 第三个原因就是生物信息是一门快速发展的学习,会出现很多新的测序方法,比如sanger测序,illumina,BGIseq,PacBio,IonTorrent,Nanopore等,每一个平台技术原理完全不同,因此数据特点也完全不同,这就需要针对每一个平台的数据做专门的学习,而且每个平台又在不断的推陈出现,可能今天你刚开发好的方法,产品升级了,都得推倒重来。还有很多新的技术,例如现在比较火的单细胞测序,Hi-C测序,Bionano测序等等内容,以后还出现更多新技术新方法,足够让你活到老,学到老。当然,你先要能活到老,吾生也有涯,而知也无涯。以有涯随无涯,殆已! 高风险才有高收益 当然啦,虽然你已经看到学习生物信息肯定是不容易了,门槛很高,但是呢,门槛高也有很多好处,就是挡住了一部分人,当你学会了,迈过门槛,你的身价就提高了。如果人人都很容易掌握了,那么也就不值钱了。所以,生物信息,前途是光明的,道路是曲折的。
用于新基因的生物信息学分析
用于新基因的生物信息 学分析 ★★★★★ reasonspare(金币+5,VIP+0):谢谢分享,欢迎常来! lwf991229(金币+0,VIP+0):置为资源帖~~ 2-9 16:12 lwf991229(金币+0,VIP+0):高亮~ 2-9 16:13 核酸序列的基本分析 运用DNAMAN软件分析核酸序列的分子质量、碱基组成和碱基分布。同时运用BioEdit(版本7.0.5.3)软件对基因做酶切谱分析。 碱基同源性分析 运用NCBI信息库的BLAST程序对基因进行碱基同源性分析(Translated query vs.protien database(blastx))网站如下:https://www.360docs.net/doc/3416133138.html,/BLAST/ 参数选择:Translated query-protein database [blastx];nr;stander1 开放性阅读框(ORF)分析 利用NCBI的ORF Finder程序对基因做开放性阅读框分析,网址如下: https://www.360docs.net/doc/3416133138.html,/projects/gorf/orfig.cgi 参数选择:Genetic Codes:1 Standard 对蛋白质序列的结构功能域分析 运用简单模块构架搜索工具(Simple Modular Architecture Research Tool,SMART)对基因的ORF出的蛋白质序列进行蛋白质结构功能域分析。该数据库由EMBL建立,其中集成了大部分目前已知的蛋白质结构功能域的数据。 网址如下:http://smart.embl-heidelberg.de/ 运用NCBI的BLAST程序再对此蛋白质序列进行rpsBlast分析 参数选择:Search Database:CDD v2.07-11937PSSM
生物信息学分析方法
核酸和蛋白质序列分析 蛋白质, 核酸, 序列 关键词:核酸序列蛋白质序列分析软 件 在获得一个基因序列后,需要对其进行生物信息学分析,从中尽量发掘信息,从而指导进一步的实验研究。通过染色体定位分析、内含子/外显子分析、ORF分析、表达谱分析等,能够阐明基因的基本信息。通过启动子预测、CpG岛分析和转录因子分析等,识别调控区的顺式作用元件,可以为基因的调控研究提供基础。通过蛋白质基本性质分析,疏水性分析,跨膜区预测,信号肽预测,亚细胞定位预测,抗原性位点预测,可以对基因编码蛋白的性质作出初步判断和预测。尤其通过疏水性分析和跨膜区预测可以预测基因是否为膜蛋白,这对确定实验研究方向有重要的参考意义。此外,通过相似性搜索、功能位点分析、结构分析、查询基因表达谱聚簇数据库、基因敲除数据库、基因组上下游邻居等,尽量挖掘网络数据库中的信息,可以对基因功能作出推论。上述技术路线可为其它类似分子的生物信息学分析提供借鉴。本路线图及推荐网址已建立超级链接,放在北京大学人类疾病基因研究中心网站(https://www.360docs.net/doc/3416133138.html,/science/bioinfomatics.htm),可以直接点击进入检索网站。 下面介绍其中一些基本分析。值得注意的是,在对序列进行分析时,首先应当明确序列的性质,是mRNA序列还是基因组序列?是计算机拼接得到还是经过PCR扩增测序得到?是原核生物还是真核生物?这些决定了分析方法的选择和分析结果的解释。 (一)核酸序列分析 1、双序列比对(pairwise alignment) 双序列比对是指比较两条序列的相似性和寻找相似碱基及氨基酸的对应位置,它是用计算机进行序列分析的强大工具,分为全局比对和局部比对两类,各以Needleman-Wunsch 算法和Smith-Waterman算法为代表。由于这些算法都是启发式(heuristic)的算法,因此并没有最优值。根据比对的需要,选用适当的比对工具,在比对时适当调整空格罚分(gap penalty)和空格延伸罚分(gap extension penalty),以获得更优的比对。 除了利用BLAST、FASTA等局部比对工具进行序列对数据库的搜索外,我们还推荐使用EMBOSS软件包中的Needle软件(http://bioinfo.pbi.nrc.ca:8090/EMBOSS/),和Pairwise BLAST (https://www.360docs.net/doc/3416133138.html,/BLAST/)。以上介绍的这些双序列比对工具的使用都比较简单,一般输入所比较的序列即可。 (1)BLAST和FASTA FASTA(https://www.360docs.net/doc/3416133138.html,/fasta33/)和BLAST (https://www.360docs.net/doc/3416133138.html,/BLAST/)是目前运用较为广泛的相似性搜索工具。这两
生物信息学(第二版)
《精要速览系列-先锋版生物信息学(第二版)》 D.R.Westhead,J.H.Parish & R.M.Twyman 科学出版社2004 A生物信息学概述 相关学习网站https://www.360docs.net/doc/3416133138.html,/inbioinformatics B数据采集 DNA,RNA和蛋白质测序 1.DNA测序原理 DNA中核苷酸的顺序是通过链式终止测序【也称为脱氧测序(dideoxy sequencing)或以发明人命名的Sanger方法】来确定。 2.DNA序列的类型 基因组DNA,是直接从基因组中得到,包括自然状态的基因 复制DNA(copy DNA, cDNA),通过反转录mRNA得到的 重组DNA,包括载体序列如质粒,修饰过的病毒和在实验室使用的其他遗传元件等 3.基因组测序策略 散弹法测序(shotgun sequence)包括随机DNA片段的生成,通过大量片段测序来覆盖整个基因组 克隆重叠群测序(clone contig)DNA片段用推理的方法亚克隆,并且进行系统的测序直到整个序列完成 4.序列质量控制 通过在DNA双链上进行多次读取完成高质量序列数据的测定 可使用如Phred等程序对最初的跟踪数据(trace data)进行碱基识别和质量判断。 载体序列和重复的DNA片段被屏蔽后,使用Phred等程序将序列拼接成重叠群 (contigs),剩下的不一致部分通过人工修饰解决 5.单遍测序 低质量的序列数据可以由单次读段(read)产生(单遍测序,single-pass sequencing)。 尽管不很准确,但单遍测序如ESTs和GSS s,可以低廉的价格快速大量的产生 6.RNA测序 因为有大量的小核苷酸(minor nucleotide)(化学改变的核苷)存在于转移RNA (tRNA)和核糖体RNA(rRNA)中,所以RNA测序不能像DNA测序那样直接进行。 需要用特殊的方法来识别被改变的核苷,包括生化实验,核磁共振谱(NRM spectroscopy)和质谱(MS)技术 7.蛋白质测序 蛋白质序列可以通过DNA序列推断得到,而RNA测序不能提供有关已改变残基或其他类型的翻译后蛋白质修饰(比如剪接或二硫键的形成) 大部分蛋白质测序是通过质谱(MS)技术进行的
生物信息学考试复习
——古 A.名词解释 1. 生物信息学:广义是指从事对基因组研究相关的生物信息的获取,加工,储存,分配,分析和解释。狭义是指综合应用信息科学,数学理论,方法和技术,管理、分析和利用生物分子数据的科学。 2. 基因芯片:将大量已知或未知序列的DNA片段点在固相载体上,通过物理吸附达到固定化(cDNA芯片),也可以在固相表面直接化学合成,得到寡聚核苷酸芯片。再将待研究的样品与芯片杂交,经过计算机扫描和数据处理,进行定性定量的分析。可以反映大量基因在不同组织或同一组织不同发育时期或不同生理条件下的表达调控情况。 3. NCBI:National Center for Biotechnology Information.是隶属于美国国立医学图书馆(NLM)的综合性数据库,提供生物信息学方面的研究和服务。 4. EMBL:European Molecular Biology Laboratory.EBI为其一部分,是综合性数据库,提供生物信息学方面的研究和服务。 5. 简并引物:PCR引物的某一碱基位置有多种可能的多种引物的混合体。 6. 序列比对:为确定两个或多个序列之间的相似性以至于同源性,而将它们按照一定的规律排列。
7. BLAST:Basic Local Alignment Search Tool.是通过比对(alignment)在数据库中寻找和查询序列(query)相似度很高的序列的工具。 8. ORF:Open Reading Frame.由起始密码子开始,到终止密码子结束可以翻译成蛋白质的核酸序列,一个未知的基因,理论上具有6个ORF。 9. 启动子:是RNA聚合酶识别、结合并开始转录所必须的一段DNA序列。原核生物启动子由上游调控元件和核心启动子组成,核心启动子包括-35区(Sextama box)TTGACA,-10区(Pribnow Box)TATAAT,以及+1区。真核生物启动子包括远上游序列和启动子基本元件构成,启动子基本元件包括启动子上游元件(GC岛,CAAT盒),核心启动子(TATA Box,+1区帽子位点)组成。 10. motif:模体,基序,是序列中局部的保守区域,或者是一组序列中共有的一小段序列模式。 11. 分子进化树:通过比较生物大分子序列的差异的数值重建的进化树。 12. 相似性:序列比对过程中用来描述检测序列和目标序列之间相似DNA碱基或氨基酸残基序列所占的比例。 同源性:两个基因或蛋白质序列具有共同祖先的结论。13.
生物信息学基本分析
核酸序列的基本分析 运用DNAMAN软件分析核酸序列的分子质量、碱基组成和碱基分布。同时运用BioEdit(版本7.0.5.3)软件对基因做酶切谱分析。 碱基同源性分析 运用NCBI信息库的BLAST程序对基因进行碱基同源性分析(Translated query vs.protien database(blastx))网站如下:https://www.360docs.net/doc/3416133138.html,/BLAST/ 参数选择:Translated query-protein database [blastx];nr;stander1 开放性阅读框(ORF)分析 利用NCBI的ORF Finder程序对基因做开放性阅读框分析,网址如下: https://www.360docs.net/doc/3416133138.html,/projects/gorf/orfig.cgi 参数选择:Genetic Codes:1 Standard 对蛋白质序列的结构功能域分析 运用简单模块构架搜索工具(Simple Modular Architecture Research Tool,SMART)对基因的ORF出的蛋白质序列进行蛋白质结构功能域分析。该数据库由EMBL建立,其中集成了大部分目前已知的蛋白质结构功能域的数据。 网址如下:http://smart.embl-heidelberg.de/ 运用NCBI的BLAST程序再对此蛋白质序列进行rpsBlast分析 参数选择:Search Database:CDD v2.07-11937PSSM Expect:0.01 Filter:Low complexity Search mode:multiple hits 1-pass 同源物种分析 用DNAMAN软件将蛋白质序列相关基因序列比对,根据结果绘出系统进化树,并进行分析。 蛋白质一级序列的基本分析 运用BioEdit(版本7.0.5.3)软件对基因ORF翻译的蛋白的一些基本性质,对分子量、等电点、氨基酸组成等作出分析。 二级结构和功能分析 信号肽预测 利用丹麦科技大学(DTU)的CBS服务器蛋白质序列的信号肽(signal peptide)预测,进入Prediction Serves 页面。 网址如下:http://www.cbs.dtu.dk/services/SignalP/ 参数选择: Eukaryotes;Both;GIF (inline);Standard; 疏水性分析 利用瑞士生物信息学研究所(Swiss Institute of Bioinformatics,SIB)的ExPASy服务器上的ProtScale程序对ORF 翻译后的氨基酸序列做疏水性分析 网址如下: https://www.360docs.net/doc/3416133138.html,/cgi-bin/protscale.pl 参数选择:
