引物设计方法(通用)

引物设计方法
设计的目的是在两个目标间取得平衡:扩增特异性和扩增效率。引物分析软件将试图通过使用每一引物设计变化的预定值在这两个目标间取得平衡。设计引用有一些需要注意的基本原理:
①引物长度
一般引物长度为18~30碱基。总的说来,决定引物退火温度(Tm值)最重要的因素就是引物的长度。有以下公式可以用于粗略计算引物的退火温度。
在引物长度小于20bp时:[4(G+C)+2(A+T)]-5℃
在引物长度大于20bp时:62.3℃+0.41℃(%G-C)-500/length-5℃
另外有许多软件也可以对退火温度进行计算,其计算原理会各有不同,因此有时计算出的数值可能会有少量差距。为了优化PCR反应,使用确保退火温度不低于54℃的最短的引物可获得最好的效率和特异性。
?xml:namespace prefix = o ns =
"urn:schemas-microsoft-com:office:office" /
总的说来,每增加一个核苷酸引物特异性提高4倍,这样,大多数应用的最短引物长度为18个核苷酸。引物长度的上限并不很重要,主要与反应效率有关。由于熵的原因,引物越长,它退火结合到靶DNA上形成供DNA聚合酶结合的稳定双链模板的速率越小。
②GC含量
一般引物序列中G+C含量一般为40%~60%,一对引物的GC含量和Tm值应该协调。若是引物存在严重的GC倾向或AT倾向则可以在引物5’端加适量的A、T或G、C尾巴。
③退火温度
退火温度需要比解链温度低5℃,如果引物碱基数较少,可以适当提高退火温度,这样可以使PCR的特异性增加;如果碱基数较多,那么可以适当减低退火温度,是DNA双链结合。一对引物的退火温度相差4℃~6℃不会影响PCR 的产率,但是理想情况下一对引物的退火温度是一样的,可以在55℃~75℃间变化。
④避免扩增模板的二级结构区域
选择扩增片段时最好避开模板的二级结构区域。用有关计算机软件可以预测估计目的片段的稳定二级结构,有助于选择模板。实验表明,待扩区域自由能(△G)小于58.6lkJ/mol时,扩增往往不能成功。若不能避开这一区域时,用7-deaza-2’-脱氧GTP取代dGTP对扩增的成功是有帮助的。
⑤与靶DNA的错配
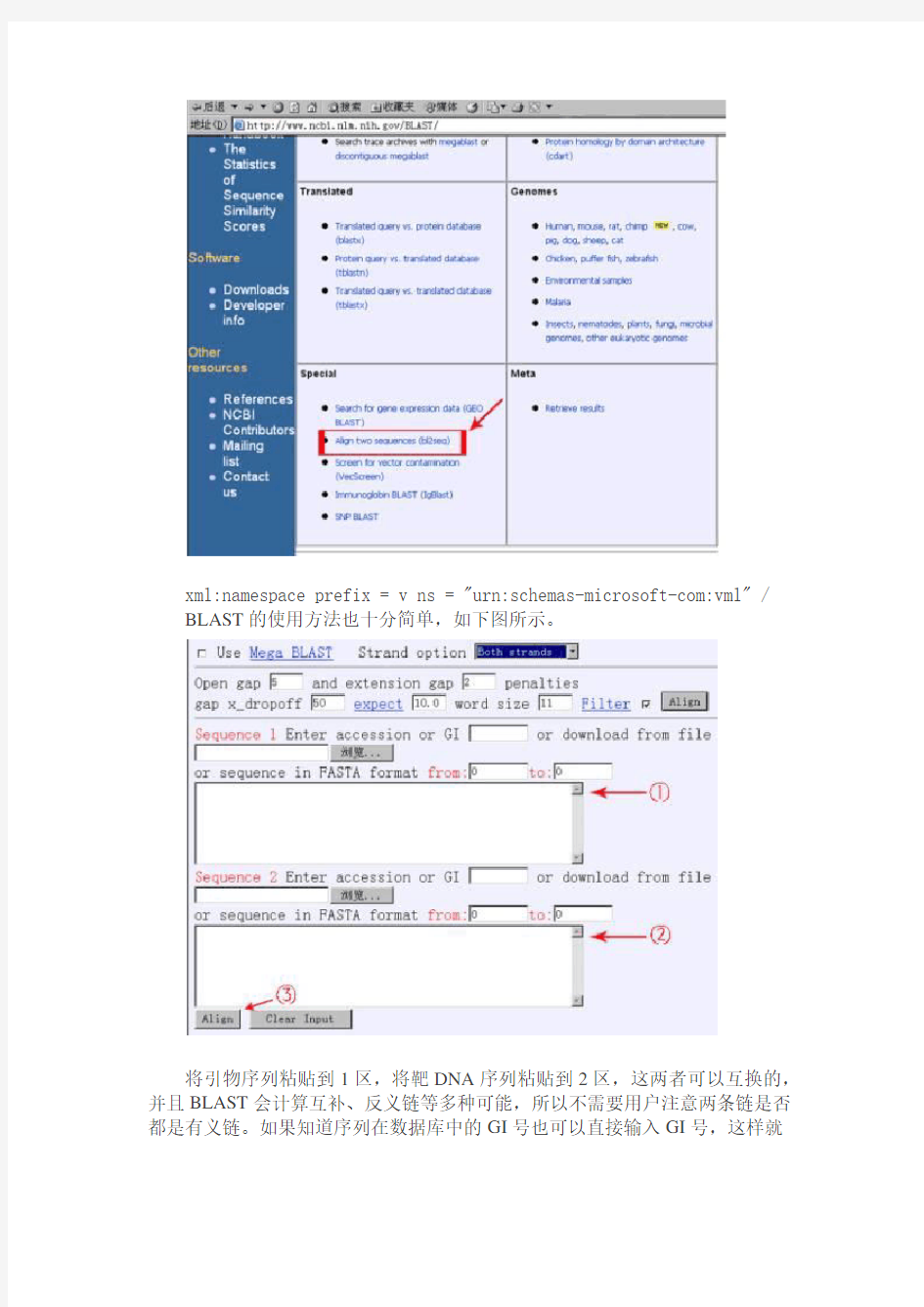
当被扩增的靶DNA序列较大的时候,一个引物就有可能与靶DNA的多个地方结合,造成结果中有多个条带出现。这个时候有必要先使用BLAST软件进行检测,网址:https://www.360docs.net/doc/804172719.html,/BLAST/。选择Align two sequences (bl2seq),如下图。
?xml:namespace prefix = v ns = "urn:schemas-microsoft-com:vml" / BLAST的使用方法也十分简单,如下图所示。
将引物序列粘贴到1区,将靶DNA序列粘贴到2区,这两者可以互换的,并且BLAST会计算互补、反义链等多种可能,所以不需要用户注意两条链是否都是有义链。如果知道序列在数据库中的GI号也可以直接输入GI号,这样就
不用粘贴一大段的序列了。最后在3处点击Align就可以查看引物在靶DNA中是否有多个同源位点了。
可是使用BLAST还是有其不方便的地方。因为它一次只能比较两条序列,那么一对引物就需要分开进行比对。如果存在错配,还需要自己计算由于错配形成的片段长度有多大。在下一篇中将介绍一个软件,可以直接将靶DNA和引物输入对产物片段进行预测。
⑥引物末端
引物3’端是延伸开始的地方,因此要防止错配就从这里开始。3’端不应超过3个连续的G或C,因这样会使引物在G+C富集序列区错误引发。3′端也不能有形成任何二级结构可能,除在特殊的PCR(AS-PCR)反应中,引物3′端不能发生错配。如扩增编码区域,引物3′端不要终止于密码子的第3位,因密码子的第3位易发生简并,会影响扩增特异性与效率。
⑦引物的二级结构
引物自身不应存在互补序列,否则引物自身会折叠成发夹状结构,这种二级结构会因空间位阻而影响引物与模板的复性结合。若用人工判断,引物自身连续互补碱基不能大于3bp。两引物之间不应该存在互补性,尤应避免3′端的互补重叠以防引物二聚体的形成。一般情况下,一对引物间不应多于4个连续碱基的同源性或互补性。
⑧为了下一步操作而产生的不完全匹配
5’端对扩增特异性影响不大,因此,可以被修饰而不影响扩增的特异性。引物5′端修饰包括:加酶切位点;标记生物素、荧光、地高辛、Eu3+等;引入蛋白质结合DNA序列;引入突变位点、插入与缺失突变序列和引入一启动子序列等。额外的碱基或多或少会影响扩增的效率,还加大引物二聚体形成的几率,但是为了下一步的操作就要作出适当的“牺牲”。
很多时候PCR只是初步克隆,之后我们还需要将目的片段亚克隆到各种载体上,那么就需要在PCR这个步骤为下一步的操作设计额外的碱基。以下总结一些为了亚克隆所要设计的序列。
a 添加限制性内切酶酶切位点
添加酶切位点是将PCR产物进行亚克隆使用得最多的手段。一般酶切位点是六个碱基,另外在酶切位点的5’端还需要加2~3个保护碱基。但是不同的酶需要的保护碱基数目是不相同的,例如:SalⅠ不需要保护碱基,EcoRⅤ需要1个,NotⅠ需要2个,Hind Ⅲ3个。其中,在原核表达设计引物时还有一些小技巧,大家可以参考:《原核表达之实验前的分析》。里面一些规则是所有表达都通用的。
有一种做法是在进行PCR反应的同时进行酶切,这样就需要注意一些内切酶在PCR反应中的酶切反应率,见附录。不过这种方法虽然方便但并不推荐。有时候,就是把PCR产物回收后酶切再与载体连接效果都不尽理想,同步进行会使出现问题的原因变得更加复杂。一旦出现问题,分析起来更麻烦。
b LIC添加尾巴
LIC的全称是Ligation-Independent cloning,它是Navogen公司专门为其部分的pET载体而发明的一种克隆方法。用LIC 法制备的pET 载体有不互补的
12–15 碱基单链粘端,与目的插入片段上相应粘端互补。扩增目的插入片段的引物5'序列要与LIC载体互补。T4 DNA 聚合酶的3'→5'外切活性经短时间即可在插入片段上形成单链粘端。由于只能由制备好的插入片段和载体互相退火形成产物,这种方法非常快速高效,而且为定向克隆。
c 定向TA克隆添加尾巴
在T载体刚出的时候大家都拍手称赞,真是方便,哪个小子脑子这么聪明想出来的。但是后来人们发现TA克隆无法将片段定向克隆到载体中,所以后来Invitrogen推出了可以定向克隆的载体,它的一端含有四个突出的碱基GTGG。因此在PCR引物设计时也要相应的加上与之互补的序列,这样片段就可以“有方向”了。
d In-Fusion克隆方法
这项技术是Clontech还属于BD的时候推出的,2004年在生物通可着实风光了一把,不但当选年度创新试剂还被大家投票为最受大家欢迎的试剂。此技术就其步骤来说是及其方便的,不需连接酶,不需长时间的反应。只要在设计引物的时候引入一段线性化载体两端的序列,然后将PCR产物和线性化的载体加入到含有BSA的In-Fusion酶溶液中,在室温下放置半个小时就可以进行转化了。这种方法特别适合大批量的转化。
这里顺便提一下如果有什么技术给大家留下深刻影响,欢迎大家发email推荐给生物通。说不定你的推荐可以让它成为年度之星呢。
如果要加入额外的碱基总是或多或少会影响到整个PCR反应,比如在加入NotⅠ的酶切位点后整个引物的退火温度就会直线上升(它识别的是8个碱基,且全为GC),这样使另外一个引物的设计变得十分困难,因为一对引物间退火温度相差不宜太远。因此上面提到许多设计原则在实际应用中往往难以做到都符合。在碰到这些情况的时候,我们只能秉着“实践是检验真理的唯一标准”这一原则,要试一试才能知道能否行得通了。
引物设计的原理与方法
引物设计的原理与方法 This model paper was revised by the Standardization Office on December 10, 2020
PCR引物设计的原理及方法 阎振鑫S111666(四川大学生命科学学院细胞生物学成都 610014) 摘要:自20世纪后期发展了PCR技术以来,PCR已经改变了整个生物学研究的进程。而PCR反应的第一步就是设计引物,引物设计的好坏直接关系到PCR的成败。PCR引物设计有许多的原则必须要遵循:引物与引物之间避免形成稳定的二聚体或发夹结构,引物与模板的序列要紧密互补。引物不能在模板的非目的位点引发DNA聚合反应等。另外,引物的设计方法也越来越多,出现了许多专门的设计软件和网站,如:PrimerPremier5.0等。 关键词:PCR 引物原理方法 NCBI PrimerPremier5.0 PCR primer design principle and method YanZhenxin (sichuan Univercity, Life science college cell biology chengdu 610014 ) Abstract: When PCR technology was find, PCR has changed all of the program in research of biology. The design of primer is the frist step of PCR. It is relation to the fate of PCR. There are some principals must be obey: dipolymer and hairpin structure must be avoid between different primers. The DNA polymerization reaction should not be triggered at the wrong site. Therefore, there are more and more methods of design primer, include the professional softwares and professional web site. Key word: PCR primer principle NCBI PrimerPremier5.0 聚合酶链式反应(Polymerase chain reaction。PCR)是20世纪后期发展起来的 一种体外扩增特异DNA片断的技术。具有快速、简便及高度敏感等优点,能极大地缩短目的基因扩增时间[1]。因此,其一直是生物学者们致力于构建cDNA文库、基因克隆以及表达调控研究的必要前提和基础[2]。PCR的第一步就是引物设计。引物设计的好坏,直接影响了PCR的结果,因此这一步很关键。成功的PCR反应既要高效,又要特异性扩增产物,因此对引物设计提出了较高的要求。引物设计需要注意的地方很多,在大多数情况下,我们都是在知道已知模板序列时进行PCR扩增的。在某些情况比如构建文库的时候也会在不知道模板序列的情况下进行设计。这个时候随机核苷酸序列
引物设计基本方法
Primer 5.0搜索引物: 1.Primer Length我常设置在18-30bp,短了特异性不好,长了没有必要。当然有特殊要求的除外,如加个酶切位点什么的。 2.PCR Product size最好是100-500bp之间,小于100bp的PCR产物琼脂糖凝胶电泳出来,条带很模糊,不好看。至于上限倒也不必要求苛刻。 3.Search parameters还是选Manual吧,Search stringency应选High,GC含量一般是40-60%。其它参数默认就可以了。 4.搜索出来的引物,按Rating排序,逐个送Oligo软件里评估。当然,搜索出的引物,其扩增产物很短,你可以不选择它,或是引物3端≥2个A或T,或引物内部连续的G或C太多,或引物3端≥2个G或C,这样的引物应作为次选,没得选了就选它。对于这样的引物,如果其它各项指标还可以,我喜欢在引物末端去掉一个不满意的或加上一个碱基,看看引物的评估参数有没有变好点。 Oligo 6.0评估引物: 1.在analyze里,Duplex Formation不管是上游引物、下游引物还是上下游引物之间,The most stable 3’-Dimer绝对值应小于4.5kcal/mol, The most stable Dimer overall绝对值一般应小于多少kcal/mol跟PCR退火温度有关,我几次实验感觉在PCR退火温度在65°的时候,The most stable Dimer ove rall 6.7kcal/mol没有问题。 2.Hairpin Formation根据黄金法则 3.False priming sites: Primer的priming efficiency应该是错配地方的4倍左右,更多当然更好。 4.在PCR栏,个人感觉其所显示的optimal annealing temperature数值值得参考。在PCR摸索条件的时候,退火温度为其数值加减2的范围就可以了。 5.Internal stability很重要:我们希望引物的内部稳定性是中间高、两边低的弧形,最起码保证3端不要过于稳定。下图1引物3端过于稳定,很容易导致不适当扩增。△G参照黄金法则,这其实很好理解:把一滴水放到大海里,这滴水就会不停的扩散分布,扩散的越厉害越稳定,所以△G绝对值越大结构越稳定。 最后说一句,敢于尝试就会成功。 第二贴 --科室工作很多,小医生了,没有办法,所以肯怕不能满足很多战友的要求(qq聊或帮助设计),在此表示抱歉。就楼上的问题我试着回答一下,不一定正确,供参考吧。 --1、两个评价系统不一样,个人感觉oligo评价引物好点,primer出来的引物,我一般按效率排序,再结合退火温度和引物长度,选择引物到oligo测试。这是初步的选择,其实引物到了oligo里,退火温度也不一样。 --2、3端的二聚体应该避免,这个要看你的退火温度决定,一个50°的退火温度肯定和65°对二聚体的影响不一样了,一般来讲尽量控制在-4.5kcal/mol以下(个人观点,很多东西真得还是需要自己摸索)。 --3、个人感觉3端有A无A影响不大,3端有T的没有经验。有T是不是一定不行,个人感觉不见得。软件是评估,法则也不是没有例外,不是1+1=2那么确定。 --4、错配和二聚体谁轻谁重,个人觉得“到致命的程度”谁都重要,我也说不好。我设计的时候,尽量两个都不得罪。 --5、GC含量并非不重要,它直接影响引物各端稳定性,3端来两个G或C,稳定性就上去了,粘在模板上很牢。所以我设计的时候,尽量避免这样的情况出现。 谈一下我学这个引物设计的过程吧:
引物的原理
引物的原理 引物是短的寡核苷酸片段,充当DNA复制的起点。因为几乎所有DNA聚合酶都不能从头合成,所以它们需要一个3’-羟基作为DNA合成的起始点。这个3’-羟基由相配的引物提供。在体内,由于DNA聚合酶的忠实性,不能从头合成DNA,因此只能由RNA聚合酶(称为引物酶)生成,采用RNA引物来延伸,在延伸过程中,RNA引物降解并由DNA 取代。在体外PCR反应中所用到的DNA引物,是根据不同的要求及模板序列设计,然后用化学法人工合成的,与模板形成双链后在DNA聚合酶的作用下就可以继续链的延伸;对于大多数PCR反应,决定整个反应成功与否的最重要因素是引物的序列和质量。 1. 不同实验要求的引物选择 在开始设计引物之前,必须弄清以下几点: (1)明确PCR的目的(例如克隆、SNP检测、定量检测等) (2)确定样品材料(基因组DNA、RNA、微小RNA) (3)确定PCR的类型(普通的、定量PCR、RT-PCR、长片段PCR),在查找序列的时候还需要考虑可能存在的问题(如假基因等) 2.引物设计的重要因素 有一些不同的软件工具可用于引物设计和引物分析。引物设计的软件如Oligo 6.22 ,Premier 5.0,Primer Express 3。引物分析常用Primer 5,Oligo 6.22,Primer-Blast。目前生工生物给客户提供的引物设计服务引物用的是在线软件Primer 3 plus, 引物长度和专一性 ?常见的引物长度为18-30个碱基。短的引物(≤15碱基)能非常高效地结合, 但是它们的专一性不够。较长的引物能提高专一性,然而退火效率低,从而导致PCR产量低下。同时应避免编码单一序列和重复序列的引物。 平衡GC含量,避免GC-和AT-富集区域 ?引物的GC含量应介于40%~60%之间。应避免聚-(dC)-或聚(dG)-区域,因为它们会降低退火反应的专一性。聚-(dA)-和聚(dT)-也应避免,因为这样会形成不稳定的引物-模板复合物,从而降低扩增效率。 3’-序列
引物设计原则
1. 引物的长度一般为15-30 bp,常用的是18-27 bp,但不应大于38,因为过长会导致其延伸温度大于74℃,不适于Taq DNA聚合酶进行反应。 2. 引物序列在模板内应当没有相似性较高,尤其是3’端相似性较高的序列,否则容易导致错配。引物3’端出现3个以上的连续碱基,如GGG或CCC,也会使错误引发机率增加。 3. 引物3’端的末位碱基对Taq酶的DNA合成效率有较大的影响。不同的末位碱基在错配位置导致不同的扩增效率,末位碱基为A的错配效率明显高于其他3个碱基,因此应当避免在引物的3’端使用碱基A。另外,引物二聚体或发夹结构也可能导致PCR反应失败。5’端序列对PCR影响不太大,因此常用来引进修饰位点或标记物。 4. 引物序列的GC含量一般为40-60%,过高或过低都不利于引发反应。上下游引物的GC含量不能相差太大。 5. 引物所对应模板位置序列的Tm值在72℃左右可使复性条件最佳。Tm值的计算有多种方法,如按公式Tm=4(G+C)+2(A+T),在Oligo软件中使用的是最邻近法(the nearest neighbor method)。 6. ΔG值是指DNA双链形成所需的自由能,该值反映了双链结构内部碱基对的相对稳定性。应当选用3’端ΔG值较低(绝对值不超过9),而5’端和中间ΔG值相对较高的引物。引物的3’端的ΔG值过高,容易在错配位点形成双链结构并引发DNA聚合反应。 7. 引物二聚体及发夹结构的能值过高(超过mol)易导致产生引物二聚体带,并且降低引物有效浓度而使PCR反应不能正常进行。 8. 对引物的修饰一般是在5’端增加酶切位点,应根据下一步实验中要插入PCR 产物的载体的相应序列而确定。 引物序列应该都是写成5-3方向的, Tm之间的差异最好控制在1度之内, 另外我觉得扩增长度大一些比较好,500bp左右。 要设计引物首先要找到DNA序列的保守区。同时应预测将要扩增的片段单链是否形成二级结构。如这个区域单链能形成二级结构,就要避开它。如这一段不能形成二级结构,那就可以在这一区域设计引物。
引物设计的11条黄金法则
引物设计的11条黄金法则
PCR引物设计的11条黄金法则 1.引物最好在模板cDNA的保守区内设计。DNA序列的保守区是通过物种间相似序列的比较确定的。在NCBI上搜索不同物种的同一基因,通过序列分析软件(比如DNAman)比对(Alignment),各基因相同的序列就是该基因的保守区。 2.引物长度一般在15~30碱基之间。 引物长度(primerlength)常用的是18-27bp,但不应大于38,因为过长会导致其延伸温度大于74℃,不适于TaqDNA聚合酶进行反应。 3.引物GC含量在40%~60%之间,Tm值最好接近72℃。 GC含量(composition)过高或过低都不利于引发反应。上下游引物的GC含量不能相差太大。另外,上下游引物的Tm值(meltingtemperature)是寡核苷酸的解链温度,即在一定盐浓度条件下,50%寡核苷酸双链解链的温度。有效启动温度,一般高于Tm值
5~10℃。若按公式Tm=4(G+C)+2(A+T)估计引物的Tm值,则有效引物的Tm为55~80℃,其Tm值最好接近72℃以使复性条件最佳。 4.引物3′端要避开密码子的第3位。 如扩增编码区域,引物3′端不要终止于密码子的第3位,因密码子的第3位易发生简并,会影响扩增的特异性与效率。 5.引物3′端不能选择A,最好选择T。 引物3′端错配时,不同碱基引发效率存在着很大的差异,当末位的碱基为A时,即使在错配的情况下,也能有引发链的合成,而当末位链为T 时,错配的引发效率大大降低,G、C错配的引发效率介于A、T之间,所以3′端最好选择T。 6.碱基要随机分布。 引物序列在模板内应当没有相似性较高,尤其是3’端相似性较高的序列,否则容易导致错误引发(Falsepriming)。降低引物与模板相似性的一种方法是,引物中四种碱基的分布最好是随机的,不要有聚嘌呤或聚嘧啶的存在。尤其3′端
引物设计的原理和程序
1 引物的设计以及初步筛选 引物的设计与初步筛选基本上通过一些分子生物学软件和相关网站来完成的,目前运用软件Primer Premier 5 或美国 whitehead 生物医学研究所基因组研究中心在因特网上提供的一款免费在线PCR引物设计程序 Primer 3来设计引物,再用软件Oligo 6进行引物评估,就可以初步获得一组比较满意的引物。但是对于初学者来说,运用软件和程序来设计引物好象无从着手,其实只要我们掌握了引物设计的基本原则和注意事项,所有问题便迎刃而解。因为无论是软件还是程序,都是以这些基本原则和注意事项为默认标准来进行引物设计的。所以,我们在进行引物设计的时候大可不必在软件和程序的参数上花费过多的时间来思考,如果没有特殊要求我们完全可以把一些参数设为默认值。下面我们主要讨论一下引物设计的原则和注意事项。 ①引物的长度一般为15-30 bp,最好在18~24 bp,因为太短易形成错配(False pr iming) 降低特异性,而太长也会降低特异性,并且降低产量[21。 ②引物在模板内最好具有单一性,也就是说在模板内部没有错配。特别是3’端,一定要避免连续4个以上的碱基互补错配。 ③引物序列的GC 含量最好在40%一60%,且上下游引物序列GC含量的差异不要太大,3’端最后5个碱基最好不要富含GC,特别是连续3个的G或C。 ④DNA双链形成所需的自由能AG,应该以5’端向3’端递减,3’端AG最好不要高于9.0 keaf mol[31。 ⑤避免形成稳定的引物二聚体(Dimer and Cross DimeO 和发夹结构(Hairpin),AG 高于4.5 keal/mol时易引发上述两种结构的产生。 ⑥引物所在的模板区域应该位于外显子区,最好跨越一个内含子区,这样便于对扩增出来的片段进行功能鉴定和表型分析。 ⑦如果以DNA为模板设计引物,产物长度在100—600 bp比较理想。而以mRNA为模板设计引物时,产物长度在150—300 bp比较理想。 ⑧5’ 端对PCR影响不太大,可以引进修饰位点和标记物[2]。只要掌握了以上原则和注意事项,我们可以在软件和程序设计的一组引物中筛选出几对我们需要的目标引物。Primer Premier 5和Oligo 6可以在https://www.360docs.net/doc/804172719.html,/soft/下载,primer3的主页位置在h ttp://https://www.360docs.net/doc/804172719.html,。 2 引物的二次筛选 引物的二次筛选是指在初次筛选出的几对引物中进一步筛选出适合我们进行特异、高效PCR扩增的那对引物。本步应注意以下两点,一是得到的一系列引物分别在Genebank 中进行回检。也就是把每条引物在比对工具(https://www.360docs.net/doc/804172719.html,/blast/) 的bl astnr中进行同源性检索,弃掉与基因组其它部分同源性比较高的引物,也就是有可能形成错配的引物。一般连续10 bp以上的同源有可能形成比较稳定的错配,特别是引物的3’端应避免连续5-6 bp的同源。二是以mRNA为模板设计引物时要先利用生物信息学的知识大致判断外显子与内含子的剪接位点(例如https://www.360docs.net/doc/804172719.html,/GENESCAN.html的GENESCA N工具或者GeneParser软,然后弃掉正好位于剪接位点的引物。
microRNA反转和定量引物设计原理、实验方法
microRNA的引物设计 以ssc-miR-222-3p为例设计引物,其成熟体序列为:AGCTACATCTGGCTACTGGGTCT 反向引物:每个反向引物的都带有一段固定的序列,可以形成一个茎环, 固定的序列为:5,-CTCAACTGGTGTCGTGGAGTCGGCAATTCAGTTGAG-3, 在这个序列后加上八个碱基,这八个碱基是ssc-miR-222-3p从后面数八个碱基的反向互补序列,就是CTGGGTCT的反向互补:AGACCCAG ,最后得到的反向引物的序列为 5,-CTCAACTGGTGTCGTGGAGTCGGCAATTCAGTTGAG AGACCCAG -3, 正向引物:每个正向引物也带有一段固定的序列,固定的序列为:ACACTCCAGCTGGG 在这个序列后加上于成熟体除后面六个外剩下的碱基序列,成熟体除掉后面六个碱基后序列为:AGCTACATCTGGCTACT 5,-ACACTCCAGCTGGG AGCTACATCTGGCTACT -3, URP:统一反向引物,也是一段固定的序列,TGGTGTCGTGGAGTCG U6引物F-CTCGCTTCGGCAGCACA ,R-AACGCTTCACGAATTTGCGT 使用方法: 1逆转的引物:所有要做的miRNA反向引物的混合,每个10微升 2PCR的引物:50微升的体系,30微升的水,10微升的正向引物,10微升的URP
2.hsa-miR-124(hsmq-0032 引物) 推荐退火温度:60℃ hsa-miR-124 扩增曲线示意图hsa-miR-124 融解曲线示意图 3.hsa-miR-125b(hsmq-0034 引物) 推荐退火温度:60℃ hsa-miR-125b 扩增曲线示意图hsa-miR-125b 融解曲线示意图
引物设计步骤与要点
引物设计step by step 1、在NCBI上搜索到目的基因,找到该基因的mRNA,在CDS选项中,找到编码区所在位置,在下面的origin中,Copy该编码序列作为软件查询序列的候选对象。 2、用Primer Premier5搜索引物 ①打开Primer Premier5,点击File-New-DNA sequence, 出现输入序列窗口,Copy目的序列在输入框内(选择As),此窗口内,序列也可以直接翻译成蛋白。点击Primer,进入引物窗口。 ②此窗口可以链接到“引物搜索”、“引物编辑”以及“搜索结果”选项,点击Search按钮,进入引物搜索框,选择“PCR primers”,“Pairs”,设定搜索区域和引物长度和产物长度。在Search Parameters里面,可以设定相应参数。一般若无特殊需要,参数选择默认即可,但产物长度可以适当变化,因为100~200bp的产物电泳跑得较散,所以可以选择300~500bp. ③点击OK,软件即开始自动搜索引物,搜索完成后,会自动跳出结果窗口,搜索结果默认按照评分(Rating)排序,点击其中任一个搜索结果,可以在“引物窗口”中,显示出该引物的综合情况,包括上游引物和下游引物的序列和位置,引物的各种信息等。 ④对于引物的序列,可以简单查看一下,避免出现下列情况:3’不要出现连续的3个碱基相连的情况,比如GGG或CCC,否则容易引起错配。此窗口中需要着重查看的包括:Tm 应该在55~70度之间,GC%应该在45%~55%间,上游引物和下游引物的Tm值最好不要相差太多,大概在2度以下较好。该窗口的最下面列出了两条引物的二级结构信息,包括,发卡,二聚体,引物间交叉二聚体和错误引发位置。若按钮显示为红色,表示存在该二级结构,点击该红色按钮,即可看到相应二级结构位置图示。最理想的引物,应该都不存在这些二级结构,即这几个按钮都显示为“None”为好。但有时很难找到各个条件都满足的引物,所以要求可以适当放宽,比如引物存在错配的话,可以就具体情况考察该错配的效率如何,是否会明显影响产物。对于引物具体详细的评价需要借助于Oligo来完成,Oligo自身虽然带有引物搜索功能,但其搜索出的引物质量感觉不如Primer5. ⑤在Primer5窗口中,若觉得某一对引物合适,可以在搜索结果窗口中,点击该引物,然后在菜单栏,选择File-Print-Current pair,使用PDF虚拟打印机,即可转换为Pdf文档,里面有该引物的详细信息。 3、用Oligo验证评估引物 ①在Oligo软件界面,File菜单下,选择Open,定位到目的cDNA序列(在primer中,该序列已经被保存为Seq文件),会跳出来两个窗口,分别为Internal Stability(Delta G)窗口和Tm窗口。在Tm窗口中,点击最左下角的按钮,会出来引物定位对话框,输入候选的上游引物序列位置(Primer5已经给出)即可,而引物长度可以通过点击Change-Current oligo length来改变。定位后,点击Tm窗口的Upper按钮,确定上游引物,同样方法定位下游引物位置,点击Lower按钮,确定下游引物。引物确定后,即可以充分利用Analyze 菜单中各种强大的引物分析功能了。
LAMP技术原理和引物设计
LAMP原理及引物设计与实例 .LAMP引物的设计 LAMP引物的设计主要是针对靶基因的六个不同的区域,基于靶基因3' 端的F3c、F2c和Flc区以及5' 端的Bl、B2和B3区等6个不同的位点设计4种引物。 FIP(Forward Inner Primer):上游内部引物,由F2区和F1C区域组成,F2区与靶基因3’端的F2c区域互补,F1C区与靶基因5' 端的Flc区域序列相同。 F3引物:上游外部引物(Forward Outer Primer),由F3区组成,并与靶基因的F3c区域互补。 BIP引物:下游内部引物(Backward Inner Primer ),由B1C和B2区域组成,B2区与靶基因3' 端的B2c区域互补,B1C域与靶基因5' 端的Blc区域序列相同. B3引物:下游外部引物(Backward Outer Primer ),由B3区域组成,和靶基因的B3c区域互补。 2.扩增原理 60-65℃是双链DNA复性及延伸的中间温度,DNA在65℃左右处于动态平衡状态。因此,DNA在此温度下合成是可能的。利用4种特异引物依靠一种高活性链置换DNA聚合酶。使得链置换DNA合成在不停地自我循环。扩增分两个阶段。 第1阶段为起始阶段,任何一个引物向双链DNA的互补部位进行碱基配对延伸时,另一条链就会解离,变成单链。上游内部引物FIP的F2序列首先与模板F2c结合(如图B所示),在链置换型DNA聚合酶的作用下向前延伸启动链置换合成。外部引物F3与模板F3c结合并延伸,置换出完整的FIP连接的互补单链(如图C所示)。FIP上的F1c与此单链上的Fl 为互补结构。自我碱基配对形成环状结构(如图C所示)。以此链为模板。下游引物BIP与B3先后启动类似于FIP和F3的合成,形成哑铃状结构的单链。迅速以3' 末端的Fl区段为起点。以自身为模板,进行DNA合成延伸形成茎环状结构。该结构是LAMP基因扩增循环的起始结构。 第2阶段是扩增循环阶段。以茎环状结构为模板,FIP与茎环的F2c区结合。开始链置换合成,解离出的单链核酸上也会形成环状结构。迅速以3’末端的B1区段为起点,以自身为模板。进行DNA合成延伸及链置换.形成长短不一的2条新茎环状结构的DNA,BIP引物上的B2与其杂交。启动新一轮扩增。且产物DNA长度增加一倍。在反应体系中添加2条环状引物LF和LB,它们也分别与茎环状结构结合启动链置换合成,周而复始。扩增的最后产物是具有不同个数茎环结构、不同长度DNA的混合物。且产物DNA为扩增靶序列的交替反向重复序列。 https://www.360docs.net/doc/804172719.html,MP的特点 LAMP与以往的核酸扩增方法相比具有如下优点: (1)操作简单,LAMP核酸扩增是在等温条件下进行,对于中小医院只需要水浴锅即可,产
microRNA(miRNA)引物设计及过程原理说明
microRNA(miRNA)引物设计及过程原理说明microRNAs的平均长度23nt左右,所以miRNA引物设计与常规引物设计存在很大差别,以下讲解一下整个miRNA引物设计的过程加上实验流程,以帮助大家对各方面的学习。 首先,引物设计之前先介绍miRNA反转录合成cDNA的过程。我们拿经典颈环序列GTCGTATCCAGTGCAGGGTCCGAGGTATTCGCACTGGAT ACGAC作介绍。打开DNAstar软件的PrimerSelect;file打开下拉菜单;打开Enter New Primer…;粘贴颈环序列;点击OK。
颈环结构已经输入,下面查看颈环结构回形成的那些发夹结构。选择颈环结构(鼠标点一下);点击Report下拉菜单;选择Primer Hairpins。 第一个发夹结构是实验所需的结构(dG=-20.4kc/m)。 下面结合has-miR-122-5P合成cDNA的具体过程讲解 has-miR-122-5P:UGGAGUGUGACAAUGGUGUUUGU 将U转T,方便后面使用:TGGAGTGTGACAATGGTGTTTGT
miRNAs的颈环结构引物:是将miRNAs的3’端后6位碱基反向互补添加到经典颈环结构的3’端形成的结构。(自己根据后面图片想一下原因,加6个碱基为经验所授) has-miR-122-5P的后6位:GTTTGT has-miR-122-5P的后6位的反向互补序列:ACAAAC 颈环引物序列: 5’-GTCGTATCCAGTGCAGGGTCCGAGGTATTCGCACTGG ATACGACACAAAC -3’ 查看形成的发夹结构(方法前面有讲) 看一下miRNA和颈环引物在一起会是怎么样子: 在含反转录酶及适当的条件下,miRNA和其颈环引物将会合成cDNA链:GTCGTATCCAGTGCAGGGTCCGAGGTATTCGCACTGGAT ACGACACAAACACCATTGTCACACTCCA
甲基化引物探针设计方法
本文叙述了一种用于甲基化分析的探针法定量PCR的引物和探针设计方法,目前用于甲基化检测的引物探针设计工具非常多,都有使用成功的案例,经过初步多方尝试,本文中叙述的为本人认为较为靠谱的方法。Oligo7的优势在于专业,参数详尽且可自由设置,模块化设计,学会后使用便利。专业的活就是要专业的用专业的工具干。
首先是进行序列转换,有较多的在线工具和联机软件都可实现,这里使用https://www.360docs.net/doc/804172719.html,/methprimer/,较为简单直观。
直接将目标序列放入如上图的编辑框中,此也可直接用于相关引物的设计,不过本人没使用过,因为不能设计探针。submit后就有转化后的序列信息,如下图: 以上详细标记了CpG位置和非CpG位置的C,可直接复制到Word标注使用,下面就可以使用Oligo7利用上边的序列设计引物和探针了,如果是设计非甲基化引物探针,则使用原始序列。
关于引物和探针的一些主要参数,主要参考invtrogen的建议: Primer设计的基本原则: a)引物长度一般在18-35mer。 b)G-C含量控制在40-60%左右。 c)避免近3’端有酶切位点或发夹结构。 d)如果可能避免在3’端最后5个碱基有2个以上的G或C。 e)如果可能避免在3’端最后1个碱基为A。 f)避免连续相同碱基的出现,特别是要避免GGGG或更多G出现。 g)退火温度Tm控制在58-60C左右。 h)如果是设计点突变引物,突变点应尽可能在引物的中间。 T aqMan 探针设计的基本原则: a)T aqMan 探针位置尽可能靠近扩增引物(扩增产物50-150bp),但不能与引物重叠。 b)长度一般为18-40mer 。 c)G-C含量控制在40-80%左右。 d)避免连续相同碱基的出现,特别是要避免GGGG或更多G出现。 e)在引物的5’端避免使用G。 f)选用比较多的碱基C。 g)退火温度Tm控制在68-70℃左右。 另:目标变异碱基最好在3’末端或3’末端-1位置,保证扩增特异性,对于甲基化,则最好是C。
引物设计的原理与方法
PCR引物设计的原理及方法 阎振鑫S111666(四川大学生命科学学院细胞生物学成都610014) 摘要:自20世纪后期发展了PCR技术以来,PCR已经改变了整个生物学研究的进程。而PCR反应的第一步就是设计引物,引物设计的好坏直接关系到PCR的成败。PCR引物设计有许多的原则必须要遵循:引物与引物之间避免形成稳定的二聚体或发夹结构,引物与模板的序列要紧密互补。引物不能在模板的非目的位点引发DNA聚合反应等。另外,引物的设计方法也越来越多,出现了许多专门的设计软件和网站,如:PrimerPremier5.0等。 关键词:PCR 引物原理方法NCBI PrimerPremier5.0 PCR primer design principle and method YanZhenxin (sichuan Univercity, Life science college cell biology chengdu 610014 ) Abstract: When PCR technology was find, PCR has changed all of the program in research of biology. The design of primer is the frist step of PCR. It is relation to the fate of PCR. There are some principals must be obey: dipolymer and hairpin structure must be avoid between different primers. The DNA polymerization reaction should not be triggered at the wrong site. Therefore, there are more and more methods of design primer, include the professional softwares and professional web site. Key word: PCR primer principle NCBI PrimerPremier5.0 聚合酶链式反应(Polymerase chain reaction。PCR)是20世纪后期发展起来的一种体外扩增特异DNA片断的技术。具有快速、简便及高度敏感等优点,能极大地缩短目的基因扩增时间[1]。因此,其一直是生物学者们致力于构建cDNA文库、基因克隆以及表达调控研究的必要前提和基础[2]。PCR的第一步就是引物设计。引物设计的好坏,直接影响了PCR的结果,因此这一步很关键。成功的PCR反应既要高效,又要特异性扩增产物,因此对引物设计提出了较高的要求。引物设计需要注意的地方很多,在大多数情况下,我们都是在知道已知模板序列时进行PCR扩增的。在某些情况比如构建文库的时候也会在不知道模板序列的情况下进行设计。这个时候随机核苷酸序列就与模板不是完全匹配。我们通常指的设计引物都是在已知模板序列的情况下进行。设计的目的是在两个目标间取得平衡:扩增特异性和扩增效率。
引物设计的原理与方法
引物设计的原理与方法 The latest revision on November 22, 2020
PCR引物设计的原理及方法 阎振鑫S111666(四川大学生命科学学院细胞生物学成都 610014) 摘要:自20世纪后期发展了PCR技术以来,PCR已经改变了整个生物学研究的进程。而PCR反应的第一步就是设计引物,引物设计的好坏直接关系到PCR的成败。PCR引物设计有许多的原则必须要遵循:引物与引物之间避免形成稳定的二聚体或发夹结构,引物与模板的序列要紧密互补。引物不能在模板的非目的位点引发DNA聚合反应等。另外,引物的设计方法也越来越多,出现了许多专门的设计软件和网站,如:PrimerPremier5.0等。 关键词:PCR 引物原理方法 NCBI PrimerPremier5.0 PCR primer design principle and method YanZhenxin (sichuan Univercity, Life science college cell biology chengdu 610014 ) Abstract: When PCR technology was find, PCR has changed all of the program in research of biology. The design of primer is the frist step of PCR. It is relation to the fate of PCR. There are some principals must be obey: dipolymer and hairpin structure must be avoid between different primers. The DNA polymerization reaction should not be triggered at the wrong site. Therefore, there are more and more methods of design primer, include the professional softwares and professional web site. Key word: PCR primer principle NCBI PrimerPremier5.0 聚合酶链式反应(Polymerase chain reaction。PCR)是20世纪后期发展起来的 一种体外扩增特异DNA片断的技术。具有快速、简便及高度敏感等优点,能极大地缩短目的基因扩增时间[1]。因此,其一直是生物学者们致力于构建cDNA文库、基因克隆以及表达调控研究的必要前提和基础[2]。PCR的第一步就是引物设计。引物设计的好坏,直接影响了PCR的结果,因此这一步很关键。成功的PCR反应既要高效,又要特异性扩增产物,因此对引物设计提出了较高的要求。引物设计需要注意的地方很多,在大多数情况下,我们都是在知道已知模板序列时进行PCR扩增的。在某些情况比如构建文库的时候也会在不知道模板序列的情况下进行设计。这个时候随机核苷酸序列
PCR引物设计原理及原则
PCR引物设计原理及原则 PCR引物设计原理 PCR引物设计的目的是为了找到一对合适的核苷酸片段,使其能有效地扩增模板DNA序列。因此,引物的优劣直接关系到PCR的特异性与成功与否。 要设计引物首先要找到DNA序列的保守区。同时应预测将要扩增的片段单链是否形成二级结构。如这个区域单链能形成二级结构,就要避开它。如这一段不能形成二级结构,那就可以在这一区域设计引物。 现在可以在这一保守区域里设计一对引物。一般引物长度为15~30碱基,扩增片段长度为100~600碱基对。 让我们先看看P1引物。一般引物序列中G+C含量一般为40%~60%。而且四种碱基的分布最好随机。不要有聚嘌呤或聚嘧啶存在。否则P1引物设计的就不合理。应重新寻找区域设计引物。 同时引物之间也不能有互补性,一般一对引物间不应多于4个连续碱基的互补。 引物确定以后,可以对引物进行必要的修饰,例如可以在引物的5′端加酶切位点序列;标记生物素、荧光素、地高辛等,这对扩增的特异性影响不大。但3′端绝对不能进行任何修饰,因为引物的延伸是从3′端开始的。这里还需提醒的是3′端不要终止于密码子的第3位,因为密码子第3位易发生简并,会影响扩增的特异性与效率。 PCR引物的设计原则: ①引物应用核酸系列保守区内设计并具有特异性。 ②产物不能形成二级结构。 ③引物长度一般在15~30碱基之间。 ④G+C含量在40%~60%之间。 ⑤碱基要随机分布。 ⑥引物自身不能有连续4个碱基的互补。 ⑦引物之间不能有连续4个碱基的互补。 ⑧引物5′端可以修饰。 ⑨引物3′端不可修饰。 ⑩引物3′端要避开密码子的第3位。 PCR引物设计的目的是找到一对合适的核苷酸片段,使其能有效地扩增模板DNA序列。如前述,引物的优劣直接关系到PCR的特异性与成功与否。对引物的设计不可能有一种包罗万象的规则确保PCR的成功,但遵循某些原则,则有助于引物的设计。 1.引物的特异性 引物与非特异扩增序列的同源性不要超过70%或有连续8个互补碱基同源。 2.避开产物的二级结构区 某些引物无效的主要原因是引物重复区DNA二级结构的影响,选择扩增片段时最好避开二级结构区域。用有关计算机软件可以预测估计mRNA的稳定二级结构,有助于选择模板。实验表明,待扩区域自由能(△G°)小于58.6lkJ/mol时,扩增往往不能成功。若不能避开这一区域时,用7-deaza-2′-脱氧GTP取代dGTP对扩增的成功是有帮助的。 3.长度 寡核苷酸引物长度为15~30bp,一般为20~27mer。引物的有效长度:Ln=2(G+C)+(A+T+,Ln值不能大于38,因为>38时,最适延伸温度会超过Taq DNA聚合酶的最适温度(74℃),不能保证产物的特异性。 4.G+C含量
PCR引物设计过程
PCR引物设计过程 (一)设计引物前应的准备工作: 1.准备载体图谱,大致准备把片断插在那个部分 2.对片断进行酶切分析,确定一下那些酶切位点不能用3.准备一本所买公司的酶的商品目录,便于查酶的各种数 据及两种酶是否可以配用 (二)引物的结构:5’—保护碱基+酶切位点+引物配对区—3’1.两个酶切位点 2.酶切位点的保护碱基 3.5’端保护碱基 4.3’端保护碱基 5.引物配对区 (三)设计引物所要考虑的问题 1.酶切位点 两个酶切位点应是载体上的,所连接片断上没有这两个位点,且距离不能太近,否则往往导致两个酶都切不好。因此,两个酶切位点要紧挨在一起,只能切一个,除非恰好是与上面两个酶在一起的酶切位点,最好隔四个核苷酸。且不能有碱基的交叉,比如AGATCTTAAG,这样的位点比较难切。2.酶的选择
最好使用双酶切效率高的,但两个酶切点最好不要是同尾酶(切下来的残基不要互补),否则效果相当于单酶切,最好使用具有共同buffer,且较常用的酶(如hind3,bamh1,ecor1等),这样可以省钱。 3.Tm的计算。 Tm是由互补的DNA区域决定的,而不互补的区域对DNA 的溶解是没有作用的。因此,对于引物的Tm,只有和模板互补的区域对Tm才有贡献。计算Tm时,只计算互补的区域(除非你的酶切位点也与模板互补)。设计引物的时候,先不管5'端的修饰序列,把互补区的Tm控制在55度以上(我喜欢控制在58以上,具体根据PCR的具体情况,对于困难的PCR,需要适当提高Tm),再加上酶切位点和保护碱基,这样的引物通常都是可用的,即使有小的问题,也可以挽回。 Tm温度高的引物就比较容易克服3’发卡、二聚体及3'非特异结合等问题。简单的计算公式可以用2+4的公式。若你计算的Tm值达到了快90 ,不包括酶切位点。引物公司给你发的单子是包括酶切位点的。自己可以再估计一下。如你设计了带酶切位点的引物,总长分别为29、33个碱基,去掉酶切位点和保护碱基,分别为17、21个碱基。引物公司给的单子是70多度,实际用的只有50度,用55度扩的结果也差不多。
PCR引物设计基本思路
PCR引物设计基本思路 1.根据实验需要,确定需要扩增的DNA序列,并知道其CDS区序列(编码结构基因区, 即从起始密码子区至终止密码子区)ncbi网站查询 RBS 149..153 /gene="eryF" CDS 158..1372 /gene="eryF" 1 ggatcccgat cgtgtcggag g aa gaggcc a agtcgcgccg ccc cgaccag ctgctggtgc 61 tgccctggat ctaccgcgac gggttcgtcg aacgcgagca ggagttcctc gctggcggcg 121 gaaagctgat cttcccccta ccccgactgg aagtcgt atg acgaccgttc ccgatctcga 181 aagcgactcc ttccacgtcg actggtaccg cacctacgcc gagctgcgcg agaccgcgcc 241 ggtgacgccg gtgcgcttcc tcggccagga cgcgtggctg gtcaccggct acgacgaggc 301 gaaggccgcg ctgagcgacc tgcgcctgag cagcgacccg aagaagaagt acccgggcgt 361 ggaggtcgag ttcccggcat acctcggttt ccccgaggac gtgcggaact acttcgccac 421 caacatgggc accagcgacc cgccgaccca cacccggctg cgcaagctgg tgtcgcagga 481 gttcaccgtc cgccgcgtgg aggcgatgcg gccccgcgtc gagcagatca ccgcggagct 541 gctcgacgag gtgggcgact ccggcgtggt cgacatcgtc gaccgcttcg cccacccgct 601 gcccatcaag gtcatctgcg agctgctcgg cgtcgacgag aagtaccgcg gggagttcgg 661 gcggtggagc tcggagatcc tggtcatgga cccggagcgg gccgaacagc gcgggcaggc 721 ggccagggag gtcgtcaact tcatcctcga cctggtcgag cgccgccgca ccgagcccgg 781 cgacgacctg ctgtccgcgc tgatcagggt ccaggacgac gatgacggtc ggctcagcgc 841 cgacgagctg acctccatcg cgctggtgct gctgctggcc ggtttcgagg cgtcggtgag 901 cctcatcggg atcggcacct acctgctgct cacccacccg gaccagctcg cgctggtgcg 961 gcgggacccg tcggcgctgc ccaacgccgt cgaggagatc ctgcgctaca tcgctccgcc 1021 ggagaccacc acgcgcttcg ccgcggagga ggtggagatc ggcggtgtcg cgatccccca 1081 gtacagcacg gtgctggtcg cgaacggcgc ggccaaccgc gacccgaagc agttcccgga 1141 cccccaccgc ttcgacgtca cccgcgacac ccgcggccac ctgtcgttcg ggcagggcat 1201 ccacttctgc atgggccggc cgctggccaa gctggagggc gaggtggcgc tgcgggcgct 1261 gttcggccgc ttccccgctc tgtcgctggg aatcgacgcc gacgacgtgg tgtggcggcg 1321 ttcgctgctg ctgcggggca tcgaccacct accggtgcgg ctcgacgga t ga gcacctgg 1381 ctgcggcggt tcggtcctcc cgtcgagcac cgggcgcggc tggtgtgctt cccgcacgcg 1441 ggagccgcgg ccgactccta cctcgacctc gcgcgcgcct tggcgcccga gatcgacgtg 1501 cacgccgtgc agtacccggg gcgccaggac cgccgcgacg aggagcccct gggcaccgcc 1561 ggcgagatcg ccgacgaggt ggccgccgtg ctgcgcgcgt cgggcggcga cggcccgttc 1621 gccctg ttcg ggcacagcat g ggcgcg ttg atcgcctacg agacggcgcg caggctcgaa 1681 cgcgagcccg gcggcgggcc gctgcggctg ttcgtgtccg ggcagaccgc cccgcgcgtg 1741 cacgagcgcc gcaccgacct gcccggcgac gacggtctgg tggacgagct gcgccggctc 1801 ggcaccagcg aggcggcgct ggccgacgag gccctgctcg ccatgtcgct gccggtgctg 1861 cgcgccgact accgcgtgct gcgctcctac gcctgggcgg acggaccacc gctgcgggcc 1921 ggcatcaccg cgctgtgcgg cgacgccgac ccgctgaccg cgaccgggga cgccgagcgc
