大肠杆菌基因型列表111
常用大肠杆菌 (K-12株来源) 的基因型

3[bTbZb KRX[NLQWXUXP_ LJ[JUXP XWURWN4grrnI>>sss=rbibpb=cmk=cl
2/01
?twv~~ ?twv~* ?twv*v
பைடு நூலகம்
bm[c;@4@9@jd]^efhZ_l n M6-* GP M,9yxx TGQF trs o N GKPDOQDCu
X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X X \ ` g iX
wr 6@KG@QGPs ;us 0OGQPFs /u 0u @KC :@JAOLLHs 3u qw*~*r 5I`]WUf]Sc A]`_[_Y5 ? HST`cSe`ci IS_fS] xKCu DCu xr ?LRKEs 9u +u @KC .@SGPs 9u =u qw*~yr LU[W_UW AAAs }}~t}~xu yr ?@KGPBFt8DOOLKs -us <GDGO@s 3u @KC 6DPPGKEs 3u qw*~{r EW_W BBs wvytww*u
批注本地保存成功开通会员云端永久保存去开通
. u*wvy{ .3012,|+/ xz~}
:QO@GK ,,z ,5xw q./yr ,6x{u{ ,62}wtw~uyxq ,=ywy -tI@ -|vv -3xy| .2w .2{ .2{l .8{vwyvp /.~|{z /.~}|} /9w|z} 2,wvw 26:w}z 36~y 36wvw 36wv{ 36wv| 36wv} 36wv~ 36wv* 36wwv 4~vx 4~vy 5/y*x 6-wv|w 6<ww~z 6<ww*y 7LS@,IRD 99w ;+8*v ;1w ;1x ;2x >5wt,IRD
大肠杆菌基因型及遗传符号说明系列一DXY

大肠杆菌基因型及遗传符号说明系列一点击次数:982 作者:佚名发表于:2009-09-27 00:00转载请注明来自丁香园来源:丁香园实验室的一般大肠杆菌拥有4288条基因,每条基因的长度约为950bp,基因间的平均间隔为118bp (基因Ⅷ)。
E.coli基因组中还包含有许多插入序列,如λ-噬菌体片段和一些其他特殊组份的片段,这些插入的片段都是由基因的水平转移和基因重组而形成的,由此表明了基因组具有它的可塑造性。
利用大肠杆菌基因组的这种特性对其进行改造,使其中的某些基因发生突变或缺失,从而给大肠杆菌带来可以观察到的变化,这种能观察到的特征叫做大肠杆菌的表现型(Phenotype),把引起这种变化的基因构成叫做大肠杆菌的基因型(Genotype)。
具有不同基因型的菌株表现出不同的特性。
分子克隆中常用的大肠杆菌及其遗传标记按Demerec等1966年提出的命名原则,采用的菌株所有的基因都假定处于野生型状态,除非在基因型上另外注明。
大肠杆菌基因型的表示方法(Demerec, et, al. 1966):一、一般规则:1、根据基因产物或其作用产物的英文名称的第一个字母缩写成3个小写斜体字母来表示。
例如:D NA Adenine Methylase→dam。
2、不同的基因座,其中任何一个突变所产生的表型变化可能相同,其表示方法是在3个小写斜体字母后加上一个斜体大写字母来表示区别。
例如:Recombination→recA、recB、recC。
3、突变位点应通过在突变基因符号后加不同数字表示。
如supE44(sup基因座E的44位突变)。
如果不知道几个等位基因中哪一/几个发生了功能性突变,则用连字符“ -”代替大写字母,如trp-31。
4、细菌的基因型中应该包含关于其携带的质粒或附加体的的信息。
这些符号包括菌株携带的质粒或附加体、质粒或附加体上的突变基因座和突变位点。
其基因符号应与基因座的表示符号明显区别,符号的第一个字母大写、不斜体并位于括号内;质粒或附加体上的突变基因座和突变位点的基因符号的表示方法与染色体上突变基因座、突变位点的符号相同。
常用大肠杆菌 (K-12株来源) 的基因型
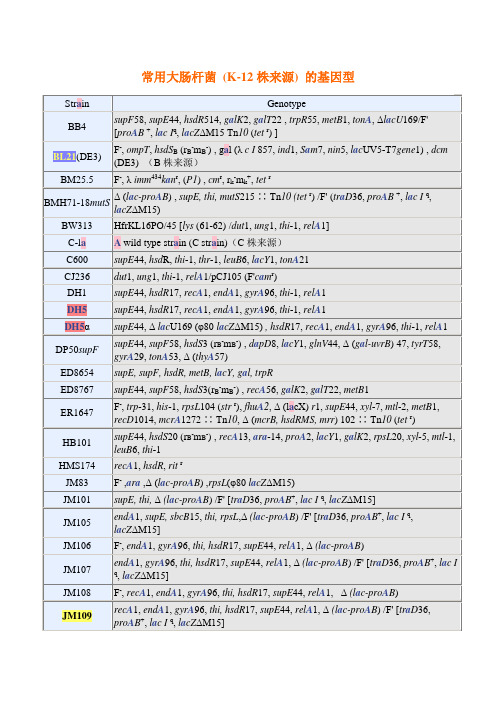
supE44,hsdR17,recA1,endA1,gyrA96,thi-1,relA1
DH5α
supE44, ΔlacU169 (φ80lacZΔM15), hsdR17,recA1,endA1,gyrA96,thi-1,relA1
DP50supF
supE44,supF58,hsdS3 (rB-mB-) ,dapD8,lacY1,glnV44, Δ (gal-uvrB) 47,tyrT58,gyrA29,tonA53, Δ (thyA57)
常用大肠杆菌(K-12株来源)的基因型
Strain
Genotype
BB4
supF58,supE44,hsdR514,galK2,galT22 ,trpR55,metB1,tonA, ΔlacU169/F' [proAB+,lac Iq,lacZΔM15 Tn10(tetr) ]
BL21(DE3)
F-,ompT,hsdSB(rB-mB-) , gal (λc I857,ind1,Sam7,nin5,lacUV5-T7gene1) ,dcm(DE3)(B株来源)
K803
F-,lacY1 or Δ (lac Iq-Y) 6 (lac-3) ,supE44,galK2,galT22,mcrA, rfbD,metB1,mcrB1,hsdR3
LE392
supE44,supF58,hsdR514,galK2,galT22,metB1,trpR55,lacY1
MC1061
hsdR, mcrB,araD139, Δ (araABCห้องสมุดไป่ตู้leu) 7679, ΔlacX74,galU, galK, rpsL, thi
MV1184
大肠杆菌基因工程菌常用类型

1、大肠杆菌DH5a菌株DH5a是世界上最常用的基因工程菌株之一。
由于DH5α是DNA酶缺陷型菌株,有利于基因克隆,保存质粒,但该菌株的蛋白酶没有缺陷,表达的蛋白容易被降解,因此通常不作为表达菌株。
E.coli DH5a在使用pUC系列质粒载体转化时,可与载体编码的β-半乳糖苷酶氨基端实现α-互补。
可用于蓝白斑筛选鉴别重组菌株。
基因型:F-,φ80dlacZΔM15,Δ(lacZYA-argF)U169,deoR,recA1,endA1,hsdR17(rk-,mk+),phoA,supE44,λ-,thi-1,gyrA96,relA12、大肠杆菌BL21(DE3) 菌株该菌株用于高效表达克隆于含有噬菌体T7启动子的表达载体(如pET系列)的基因。
T7噬菌体RNA聚合酶位于λ噬菌体DE3区,该区整合于BL21的染色体上。
该菌适合表达非毒性蛋白。
基因型:F-,ompT,hsdS(rBB-mB-),gal,dcm(DE3)3、大肠杆菌BL21(DE3) pLysS菌株该菌株含有质粒pLysS,因此具有氯霉素抗性。
PLysS含有表达T7溶菌酶的基因,能够降低目的基因的背景表达水平,但不干扰目的蛋白的表达。
该菌适合表达毒性蛋白和非毒性蛋白。
基因型:F-,ompT hsdS(rBB-mB-),gal,dcm(DE3,pLysS ,Camr4、大肠杆菌JM109菌株该菌株在使用pUC系列质粒载体进行DNA转化或用M13 phage载体进行转染时,由于载体DNA产生的LacZa多肽和JM09编码的LacZΔM15进行α-互补,从而显示β-半乳糖苷酶活性,由此很容易鉴别重组体菌株。
基因型:recA1,endA1,gyrA96,thi-1,hsdR17,supE44,relA1,Δ(lac-proAB)/F’[traD36,proAB+,lacIq,lacZΔM15]5、大肠杆菌TOP10菌株该菌株适用于高效的DNA克隆和质粒扩增,能保证高拷贝质粒的稳定遗传。
细菌菌株基因型及基因符号说明

大肠杆菌基因型及遗传符号说明前言:实验室的一般大肠杆菌拥有4288条基因,每条基因的长度约为950bp,基因间的平均间隔为118bp(基因Ⅷ)。
E.coli基因组中还包含有许多插入序列,如λ-噬菌体片段和一些其他特殊组份的片段,这些插入的片段都是由基因的水平转移和基因重组而形成的,由此表明了基因组具有它的可塑造性。
利用大肠杆菌基因组的这种特性对其进行改造,使其中的某些基因发生突变或缺失,从而给大肠杆菌带来可以观察到的变化,这种能观察到的特征叫做大肠杆菌的表现型(Phenotype),把引起这种变化的基因构成叫做大肠杆菌的基因型(Genotype)。
具有不同基因型的菌株表现出不同的特性。
分子克隆中常用的大肠杆菌及其遗传标记按Demerec等1966年提出的命名原则,采用的菌株所有的基因都假定处于野生型状态,除非在基因型上另外注明。
大肠杆菌基因型的表示方法(Demerec, et, al. 1966):一、一般规则:1、根据基因产物或其作用产物的英文名称的第一个字母缩写成3个小写斜体字母来表示。
例如:DNA Adenine Methylase→dam。
2、不同的基因座,其中任何一个突变所产生的表型变化可能相同,其表示方法是在3个小写斜体字母后加上一个斜体大写字母来表示区别。
例如:Recombination→recA、recB、recC。
3、突变位点应通过在突变基因符号后加不同数字表示。
如supE44(sup基因座E的44位突变)。
如果不知道几个等位基因中哪一/几个发生了功能性突变,则用连字符“-”代替大写字母,如trp-31。
4、细菌的基因型中应该包含关于其携带的质粒或附加体的的信息。
这些符号包括菌株携带的质粒或附加体、质粒或附加体上的突变基因座和突变位点。
其基因符号应与基因座的表示符号明显区别,符号的第一个字母大写、不斜体并位于括号内;质粒或附加体上的突变基因座和突变位点的基因符号的表示方法与染色体上突变基因座、突变位点的符号相同。
各种大肠杆菌菌株特点

各种大肠杆菌菌株特点1:DH5a菌株DH5a是一种常用于质粒克隆的菌株。
E.coli DH5a在使用pUC系列质粒载体转化时,可与载体编码的β-半乳糖苷酶氨基端实现α-互补。
可用于蓝白斑筛选鉴别重组菌株。
基因型:F-,φ80dlacZΔM15,Δ(lacZYA-argF)U169,deoR,recA1,endA1,hsdR17(rk-,mk+),phoA,supE44,λ-,thi-1,gyrA96,relA12:BL21(DE3) 菌株该菌株用于高效表达克隆于含有噬菌体T7启动子的表达载体(如pET系列)的基因。
T7噬菌体RNA聚合酶位于λ 噬菌体DE3区,该区整合于BL21的染色体上。
该菌适合表达非毒性蛋白。
基因型:F-,ompT,hsdS(rBB-mB-),gal,dcm(DE3)3:BL21(DE3) pLysS菌株该菌株含有质粒pLysS,因此具有氯霉素抗性。
PLysS含有表达T7溶菌酶的基因,能够降低目的基因的背景表达水平,但不干扰目的蛋白的表达。
该菌适合表达毒性蛋白和非毒性蛋白。
基因型:F-,ompT hsdS(rBB-mB-),gal,dcm(DE3,pLysS ,Camr4:JM109菌株该菌株在使用pUC系列质粒载体进行DNA转化或用M13 phage载体进行转染时,由于载体DNA产生的LacZa多肽和JM09编码的LacZΔM15进行α-互补,从而显示β-半乳糖苷酶活性,由此很容易鉴别重组体菌株基因型:recA1,endA1,gyrA96,thi-1,hsdR17,supE44,relA1,Δ(lac-proAB)/F’5:TOP10菌株该菌株适用于高效的DNA克隆和质粒扩增,能保证高拷贝质粒的稳定遗传。
基因型:F- ,mcrAΔ(mrr-hsd RMS-mcrBC),φ80 ,lacZΔM15,△lacⅩ74,recA1 ,araΔ139Δ(ara-leu)7697,galU ,galK ,rps,(Strr) endA1,nupG6:HB101菌株该菌株遗传性能稳定,使用方便,适用于各种基因重组实验基因型:supE44,hsdS20(rB-mB-),recA13,ara-14,proA2,lacY1,galK2,rpsL20,xyl-5,mtl-1,leuB6,thi-17:M110或SCS110大多数大肠杆菌菌株中含有Dam甲基化酶和Dcm甲基化酶,前者可以在GATC序列中腺嘌呤N-6位上引入甲基,后者在CCA/TGC序列的第一个胞嘧啶 C-5位置上引入甲基。
大肠杆菌的基因型-概述说明以及解释

大肠杆菌的基因型-概述说明以及解释1.引言1.1 概述大肠杆菌是一种常见的革兰氏阴性杆菌,属于肠道菌群中的重要成员。
它在自然界和人体内广泛存在,并且具有广泛的基因型多样性。
这使得大肠杆菌成为了微生物遗传学和进化生物学领域的研究模型。
在大肠杆菌中,基因型是指该菌株拥有的基因组合和基因的分布情况。
大肠杆菌的基因型可以通过不同的方法进行分类和鉴定。
目前主要的分类方法包括单核苷酸多态性分析、基因片段分析和全基因组测序等。
通过这些方法,我们可以更全面地了解大肠杆菌的基因型组成和种群结构。
大肠杆菌的基因型在其功能和特点方面具有重要意义。
大肠杆菌是一种典型的益生菌,它在人体内具有多种有益作用,包括帮助消化吸收、维持肠道稳定性和参与免疫调节等。
不同基因型的大肠杆菌可能具有不同的功能特点,比如某些基因型可能携带耐药基因或致病因子,导致感染和疾病的发生。
因此,对大肠杆菌基因型的研究有助于我们深入了解其功能机制和生态适应能力。
总之,大肠杆菌作为一种常见的菌株,其基因型具有多样性和重要性。
通过研究大肠杆菌的基因型,我们可以深入探索其功能特点和生态适应能力,进一步促进微生物遗传学和进化生物学的研究。
未来,我们可以通过结合多样的研究方法和技术,进一步挖掘和解析大肠杆菌基因型的奥秘,并探索其在人体健康和疾病中的作用。
文章结构是指文章部分之间的逻辑关系和组织,它有助于读者理解文章的内容和思路。
本文的结构如下:1. 引言1.1 概述1.2 文章结构1.3 目的2. 正文2.1 大肠杆菌的基因型分类2.2 大肠杆菌基因型的功能和特点3. 结论3.1 大肠杆菌基因型的重要性3.2 未来研究的方向文章结构部分是为了描述本文的组织结构,它有助于读者了解文章的内容安排和逻辑关系。
在本文中,我们首先介绍引言部分,包括概述、文章结构和目的。
在概述中,我们简要介绍了大肠杆菌的基因型。
在文章结构中,我们明确了本文的结构和章节安排,帮助读者理解文章的整体框架。
细菌基因型及其基因符号1102

大肠杆菌基因型及遗传符号说明前言:实验室的一般大肠杆菌拥有4288条基因,每条基因的长度约为950bp,基因间的平均间隔为118bp(基因Ⅷ)。
E.coli基因组中还包含有许多插入序列,如λ-噬菌体片段和一些其他特殊组份的片段,这些插入的片段都是由基因的水平转移和基因重组而形成的,由此表明了基因组具有它的可塑造性。
利用大肠杆菌基因组的这种特性对其进行改造,使其中的某些基因发生突变或缺失,从而给大肠杆菌带来可以观察到的变化,这种能观察到的特征叫做大肠杆菌的表现型(Phenotype),把引起这种变化的基因构成叫做大肠杆菌的基因型(Genotype)。
具有不同基因型的菌株表现出不同的特性。
分子克隆中常用的大肠杆菌及其遗传标记按Demerec等1966年提出的命名原则,采用的菌株所有的基因都假定处于野生型状态,除非在基因型上另外注明。
大肠杆菌基因型的表示方法(Demerec, et, al. 1966):一、一般规则:1、根据基因产物或其作用产物的英文名称的第一个字母缩写成3个小写斜体字母来表示。
例如:DNA Adenine Methylase→dam。
2、不同的基因座,其中任何一个突变所产生的表型变化可能相同,其表示方法是在3个小写斜体字母后加上一个斜体大写字母来表示区别。
例如:Recombination→recA、recB、recC。
3、突变位点应通过在突变基因符号后加不同数字表示。
如supE44(sup基因座E的44位突变)。
如果不知道几个等位基因中哪一/几个发生了功能性突变,则用连字符“-”代替大写字母,如trp-31。
4、细菌的基因型中应该包含关于其携带的质粒或附加体的的信息。
这些符号包括菌株携带的质粒或附加体、质粒或附加体上的突变基因座和突变位点。
其基因符号应与基因座的表示符号明显区别,符号的第一个字母大写、不斜体并位于括号内;质粒或附加体上的突变基因座和突变位点的基因符号的表示方法与染色体上突变基因座、突变位点的符号相同。
- 1、下载文档前请自行甄别文档内容的完整性,平台不提供额外的编辑、内容补充、找答案等附加服务。
- 2、"仅部分预览"的文档,不可在线预览部分如存在完整性等问题,可反馈申请退款(可完整预览的文档不适用该条件!)。
- 3、如文档侵犯您的权益,请联系客服反馈,我们会尽快为您处理(人工客服工作时间:9:00-18:30)。
A listed gene name means that gene carries a loss of function mutation, a Δ preceding a gene name means the gene is deleted. If a gene is not listed, it is not known to be mutated. Prophages present in wt K-12 strains (F, λ, e14, rac) are listed only if ab sent. E. coliB strains are naturally lon- and dcm-.F- = Does not carry the F plasmidF+ = Carries the F plasmid. The cell is able to mate with F- through conjugation.F'[ ] = Carries an F plasmid that has host chromosomal genes on it from a previous recombination event. This cell can also mate with F- through conjugation. Chromosomal genes carried in the F plasmid are listed in brackets.rB/K+/- = The (B/K) defines the strain lineage. The +/- indicates whether the strain has or hasn't got the restriction system.mB/K+/- = The (B/K) defines the strain lineage. The +/- indicates whether the strain has or hasn't got the modification (methylation) system.hsdS = Both restriction and methylation of certain sequences is deleted from the strain. If you transform DNA from such a strain into a wild type strain, it will be degraded.hsdR = For efficient transformation of cloned unmethylated DNA from PCR amplificationsINV( ) = chromosomal inversion between locations indicatedahpC = mutation to alkyl hydroperoxide reductase conferring disulfide reductase activityara-14 = cannot metabolize arabinosearaD = mutation in L-ribulose-phosphate 4-epimerase blocks arabinose metabolismcycA = mutation in alanine transporter; cannot use alanine as a carbon sourcedapD = mutation in succinyl diaminopimelate aminotransferase leads to succinate or (lysine + methionine) requirementΔ( ) = chromosomal deletion of genes between the listed genes (may include unlisted genes!) dam = adenine methylation at GATC sequences abolished; high recombination efficiency; DNA repair turned ondcm = cytosine methylation at second C of CCWGG sites abolisheddeoR = regulatory gene that allows constitutive expression of deoxyribose synthesis genes; permits uptake of large plasmids. See Hanahan D, US Patent 4,851,348. ***This has been called into question, as the DH10B genome sequence revealed that it is deoR+. See Durfee08, PMID 18245285.dnaJ = one of the chaparonins inactivated; stabilizes some mutant proteinsdut1 = dUTPase activity abolished, leading to increased dUTP concentrations, allowing uracil instead of thymine incorporation in DNA. Stable U incorporation requires ung gene mutation as well.endA1 = For cleaner preparations of DNA and better results in downstream applications due to the elimination of non-specific digestion by Endonuclease I(e14) = excisable prophage like element containing mcrA gene; present in K-12 but missing in many other strainsgalE = mutations are associated with high competence, increased resistance to phage P1 infection, and 2-deoxygalactose resistance. galE mutations block the production of UDP-galactose, resulting in truncation of LPS glycans to the minimal, "inner core". The exceptional competence of DH10B/TOP10 is thought to be a result of a reduced interference from LPS in the binding and/oruptake of transforming DNA. galE15 is a point mutation resulting in a Ser123 -> Phe conversion near the enzyme's active site. See van Die, et al. PMID 6373734, Hanahan, et al. PMID 1943786, and EcoSal ISBN 1555811647. --Dcekiert 16:56, 23 January 2008 (CST)galk = mutants cannot metabolize galactose and are resistant to 2-deoxygalactose. galK16 is an IS2 insertion ~170bp downstream of the galK start codon. See EcoSal ISBN 1555811647. --Dcekiert 16:56, 23 January 2008 (CST)galU = mutants cannot metabolize galactosegor = mutation in glutathione reductase; enhances disulphide bond formationglnV = suppression of amber (UAG) stop codons by insertion of glutamine; required for some phage growthgyrA96 = mutation in DNA gyrase; conveys nalidixic acid resistancegyrA462 = mutation in DNA gyrase; conveys resistance to ccdB colicin gene producthflA150 = protease mutation stabilizing phage cII protein; high frequency of lysogenization by λ Δ(lac)X74 = Deletion of the entire lac operon as well as some flanking DNA.lacIq or lacIQ = overproduction of the lac repressor protein; -35 site in promoter upstream of lacI is mutated from GCGCAA to GTGCAAlacIQ1 = overproduction of the lac repressor protein; contains a 15 bp deletion to create optimal -35 site in promoter upstream of lacIlacY = deficient in lactose transport; deletion of lactose permease (M protein)lacZΔM15 = partial deletion of the lacZ gene that allows α complementation of the β-galactosidase gene; required for blue/white selection on XGal plates. Deletes the amino portion of lacZ (aa 11-41).leuB = requires leucineΔlon = deletion of the lon proteasemalA = cannot metabolize maltosemcrA = Mutation eliminating restriction of DNA methylated at the sequence CmCGG (possibly mCG). Carried on the e14 prophage (q.v.)mcrB = Mutation eliminating restriction of DNA methylated at the sequence RmCmetB = requires methioninemetC = requires methioninemrr = Mutation eliminating restriction of DNA methylated at the sequence CmAG or GmAC mtlA = cannot metabilize mannitol(Mu) = Mu prophage present. Muδ means the phage is defective.mutS - mutation inhibits DNA repair of mismatches in unmethylated newly synthesized strands nupG = same as deoRompT = mutation in outer membrane protein protease VII, reducing proteolysis of expressed proteins(P1) = Cell carries a P1 prophage. Cells express the P1 restriction system.(P2) = Cell carries a P2 prophage. Allows selection against Red+ Gam+ λ(φ80) = Cell carries the lambdoid prophage φ80. A defective version of this phage car rying lacZM15 deletion (as well as wild-type lacI, lacYA, and flanking sequences) is present in some strains. The φ80 attachment site is just adjacent to tonB.pLysS = contains pLysS plasmid carrying chloramphenicol resistance and phage T7 lysozyme, effective at attenuating activity of T7 RNA polymerase, for better inhibition of expression undernon-induced conditions. The sequence can be found here.proA/B = requires prolinerecA1 = For reduced occurrence of unwanted recombination in cloned DNA; cells UV sensitive, deficient in DNA repairrecA13 = as for recA1, but inserts less stable.recBCD = Exonuclease V; mutation in RecB or RecC reduces general recombination by a factor of 100; impaired DNA repair; UV sensitive, easier propagation of inverted repeatsrecJ Exonuclease involved in alternate recombinationrelA = relaxed phenotype; permits RNA synthesis in absence of protein synthesisrha = blocked rhamose metabolismrnc = encodes RnaseIII (rnc-14 is a common null mutant)rne = encodes RnaseE (rne-3071 is a common temperature sensitive mutant)rpsL = mutation in ribosomal protein S12 conveying streptomycin resistance; also called strA sbcBC = ExoI activity abolished; usually present in recBC strains; recombination proficient, stable inverted repeatssr1 = cannot metabolize sorbitolsupE = glnVsupF = tyrTthi = requires thiaminethyA = requires thymidineTn10 = transposon normally carrying Tetracycline resistanceTn5 = transposon normally carrying Kanamycin resistancetonA = Mutation in outer membrane protein conveying resistance to phage T1 and phage T5traD = Mutation eliminating transfer factor; prevents transfer of F plasmidtrxB = mutation in thioredoxin reductase; enhances disulphide bond formation in the cytoplasm tsx = outer membrane protein mutation conveying resistance to phage T6 and colicin KtryT = suppression of amber (UAG) stop codons by insertion of tyrosine; needed for some phage infection such as λgt11.ung1 = allows uracil to exist in plasmid DNAxyl-5 = blocked xylose metabolismSmR = Streptomycin resistance。
